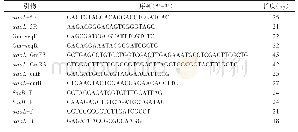
《表3 CRISPR-Cpf1系统基因敲除所用的引物》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《谷氨酸棒状杆菌CRISPR-Cpf1和Cre/loxP基因敲除技术的比较》
以敲除谷氨酸棒状杆菌ATCC 13032基因组的argR为例,CRISPR-Cpf1系统敲除质粒的构建步骤如下。首先以pJYS3_ΔcrtYf质粒为模板,以crtYf-F-1/crtYf-R-1为引物进行定点突变,通过全质粒PCR将crtYf基因的crRNA序列(5′-GAATTTCT ACTGTTGTAGATCAGGCAACCATAGGGCAGGA A-3′)替换为argR基因的cr RNA序列(5′-GAATTTC TACTGTTGTAGATTACAGATCATTCCGGCAACA TCGC-3′)以及argF的crRNA序列(5′-GAATTTCTA CTGTTGTAGATGTCCCTCGAGTGGACGCTCCG-3′),然后用Dpn I限制性内切酶消化母本质粒。取3μL消化后的PCR产物通过化学转化法转化到E.coli JM109感受态细胞中,待其长出菌落进行PCR验证并测序验证,得到质粒pJYS3_ΔcrtYf-1。再以pJYS3_ΔcrtYf-1为模板,以cr RNA_argR-F/cr RNA_argR-R为引物,通过PCR扩增得到除去crtYf基因上下游同源臂的A片段。再以谷氨酸棒状杆菌ATCC 13032基因组为模板,分别以arg R-F-F/arg R-F-R和argR-R-F/argR-R-R为引物扩增argR的上游和下游同源片段,并将A片段、arg R的上游和下游同源片段进行连接,取5μL连接液热转化至E.coli JM109感受态细胞,待其长出菌落后,以arg R-F-F/arg R-F-R为引物进行菌落PCR和基因测序验证,其中验证正确的打靶质粒命名为pJYS3_ΔargR。具体构建流程如图2所示。其中引物设计见表3。
| 图表编号 | XD0043794100 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.02.20 |
| 作者 | 占米林、阚宝军、张辉、董晋军、许国超、韩瑞枝、倪晔 |
| 绘制单位 | 江南大学生物工程学院工业生物技术教育部重点实验室、江南大学生物工程学院工业生物技术教育部重点实验室、江南大学生物工程学院工业生物技术教育部重点实验室、江南大学生物工程学院工业生物技术教育部重点实验室、江南大学生物工程学院工业生物技术教育部重点实验室、江南大学生物工程学院工业生物技术教育部重点实验室、江南大学生物工程学院工业生物技术教育部重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |