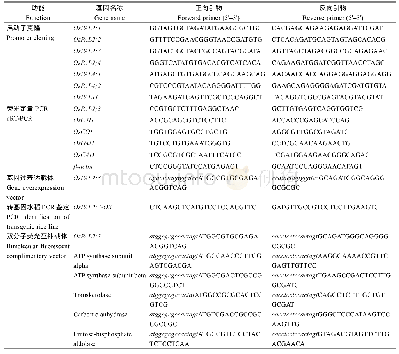
《表1 本研究所用到的引物》
带星号(*)的标记参考Yoshioka等[18]2017年发表的文献。
采用CTAB法提取SL-F2群体叶片DNA[31],利用SSRLocator软件[32]及内置的Primer 3程序进行SSR搜索与引物设计,参考Li等[33]采用CAPS/dCAPS Designer基于Wheat660K SNP芯片开发的标记进行修改完成CAPS和dCPAS标记的开发,所用标记的信息如表1所示,所有引物均由北京博迈德基因技术有限公司合成。PCR扩增体系总体积为20μL,包括50 ng模板DNA,0.2μmol L–1引物和1×Taq M a s t e r M i x(江苏康为世纪生物科技有限公司,CW0682L,包含0.2 mmol L–1 dNTPs、0.15 mmol L–1MgCl2和1 U Taq DNA聚合酶)。PCR扩增采用94℃预变性5 min,然后按照94℃变性30 s,55℃退火30 s(对于个别引物需根据具体情况调节退火温度),72℃延伸30 s(对于EST标记,延伸时间延长至2 min)的条件进行35个循环,最后72℃延伸10 min。SSR标记在PCR扩增后直接进行电泳,CAPS标记、dCAPS标记及EST标记在PCR扩增后采用相应的限制性内切酶酶切后电泳检测。限制性内切酶(美国NEB公司,购自生工生物工程 (上海)股份有限公司) 的酶切反应按照相应说明书进行。对于SSR标记PCR扩增产物和dCAPS标记的酶切产物,用8%非变性聚丙烯酰胺凝胶电泳进行分离,而CAPS标记与EST标记的PCR产物和酶切产物用2%琼脂糖凝胶电泳分离检测。
| 图表编号 | XD0078520000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.06.12 |
| 作者 | 金迪、王冬至、王焕雪、李润枝、陈树林、阳文龙、张爱民、刘冬成、詹克慧 |
| 绘制单位 | 河南农业大学农学院、中国科学院遗传与发育生物学研究所、植物细胞与染色体工程国家重点实验室、北京农学院植物科学技术学院、北京农学院植物科学技术学院、河南农业大学农学院、中国科学院遗传与发育生物学研究所、植物细胞与染色体工程国家重点实验室、中国科学院遗传与发育生物学研究所、植物细胞与染色体工程国家重点实验室、中国科学院遗传与发育生物学研究所、植物细胞与染色体工程国家重点实验室、北京科技大学生物与农业研究中心、河南农业大学农学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式