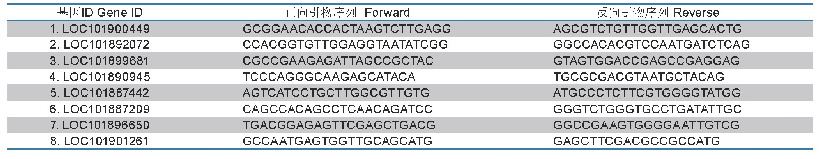
《表2 裂皮鹅膏转录组MSDIN基因序列验证的特异性引物》
以“MSDIN”已知序列为检索条件比对,在U-nig-ene编码的氨基酸序列中进行搜索,得到符合条件的多肽氨基酸序列及Unigene编号,由Unigene编号获得相应的CDS序列。根据CDS序列在两边设计特异性引物(表2),以裂皮鹅膏cDNA为模板进行PCR扩增和测序,验证MSDIN家族基因序列的正确性。PCR体系如下:20μL反应体系:200 ng/μL的cDNA模板1μL,10μmol/L上下游引物各1μL,PCR酶(1.25 U/μL)0.5μL,2×Mix 10μL(Tks Gflex TM DNA Polymerase Low DNA,TaKaRa),加水补齐至20μL。反应条件(采用Touchdown方法):94℃预热4 min;94℃变性30 s,62℃退火20 s,72℃延伸30 s,5个循环;94℃变性30 s,55℃退火20 s,72℃延伸30 s 10个循环;94℃变性30 s,53℃退火20 s,72℃延伸30 s 20个循环(退火温度每一个循环降0.2℃)。PCR产物经切胶回收后连接到pUC19-T载体(TaKaRa),并转化大肠杆菌感受态细胞。挑选3~6个正确的转化子送华大基因进行测序验证。
| 图表编号 | XD0062455600 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.06.25 |
| 作者 | 贺勇、张成花、邓旺秋、李泰辉、周小云 |
| 绘制单位 | 湖南农业大学生物科学技术学院、广东省科学院广东省微生物研究所华南应用微生物国家重点实验室广东省菌种保藏与应用重点实验室、广东省科学院广东省微生物研究所华南应用微生物国家重点实验室广东省菌种保藏与应用重点实验室、湖南农业大学生物科学技术学院、广东省科学院广东省微生物研究所华南应用微生物国家重点实验室广东省菌种保藏与应用重点实验室、广东省科学院广东省微生物研究所华南应用微生物国家重点实验室广东省菌种保藏与应用重点实验室、湖南农业大学生物科学技术学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式