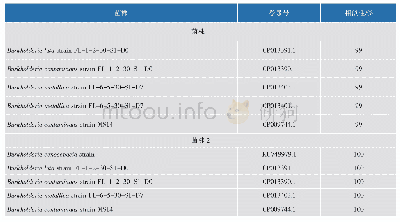
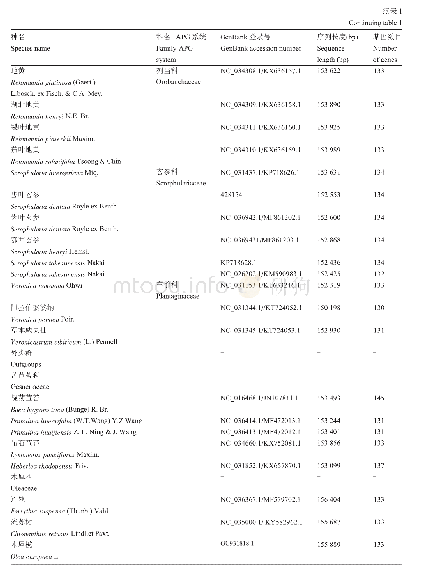
《表3 来源于GeneBank和文献的MSDIN前体肽序列信息》
本研究中用于MSDIN家族聚类分析的前体多肽序列一共有42条,其中包含14条从NCBI数据库检索得到的前体多肽序列,4条来源于毒鹅膏基因组分析数据的前体肽序列(Pulman et al.,2016),以及24条从裂皮鹅膏转录组数据中检索并经反转录验证后获得的MSDIN多肽序列(表1;表3)。所有序列使用ClustalW进行比对后,对需要调整的序列进行手工调整,然后利用MEGA 6.0(Tamura et al.,2013)采用最大似然法(ML)进行建树分析,Bootshrap设置为1 000,利用MEGA中提供的替代模型测试选择Jones-Taylor-Thornton作为本次建树的最佳进化模型,位点之间采用Gamma分布,含有Gaps或缺失数据高于5%的位点则选择部分删除(位点覆盖截止为95%),进化树上只显示高于50%的支持率。
| 图表编号 | XD0062455700 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.06.25 |
| 作者 | 贺勇、张成花、邓旺秋、李泰辉、周小云 |
| 绘制单位 | 湖南农业大学生物科学技术学院、广东省科学院广东省微生物研究所华南应用微生物国家重点实验室广东省菌种保藏与应用重点实验室、广东省科学院广东省微生物研究所华南应用微生物国家重点实验室广东省菌种保藏与应用重点实验室、湖南农业大学生物科学技术学院、广东省科学院广东省微生物研究所华南应用微生物国家重点实验室广东省菌种保藏与应用重点实验室、广东省科学院广东省微生物研究所华南应用微生物国家重点实验室广东省菌种保藏与应用重点实验室、湖南农业大学生物科学技术学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式