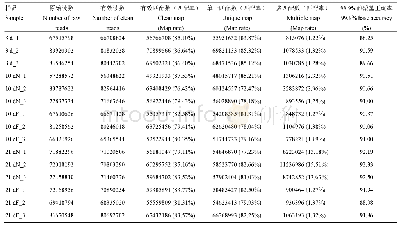
《表3 RNA-seq Map统计》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《基于转录组测序对小麦抗叶锈性相关基因的筛选与分析》
注:Useful Reads:用于比对的序列总数;Map events count:比对事件总数;Total Mapped reads:比对上参考基因组的序列总数;Total Mapped:比对上参考基因组的序列所占百分比;Multiple Mapped reads:比对到多个位置的序列总数;Multiple Mapped%:比对到多个位置的序列所
通过Bowtie2建立参考基因组索引,然后使用Tophat2(http://tophat.cbcb.umd.edu/)将过滤后的Reads比对到参考基因组上。0、1和6 d样本比对上参考基因组的序列总数分别为34 275 708、33 853 145和37 746 006,比对上参考基因组的序列所占百分比分别为71.66%、72.14%和83.01%(表3)。以上分析结果表明,试验所产生的测序序列的Mapping比例都高于70%,Mapping成功,转录组测序参考基因组选择合适,且相关实验不存在污染。
| 图表编号 | XD00129896100 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.01.01 |
| 作者 | 张艳俊、杨毅清、袁心悦、王海燕、刘大群 |
| 绘制单位 | 河北农业大学植物保护学院、河北省农作物病虫害生物防治工程技术研究中心、国家北方山区农业工程技术研究中心、河北农业大学植物保护学院、河北省农作物病虫害生物防治工程技术研究中心、国家北方山区农业工程技术研究中心、河北农业大学植物保护学院、河北省农作物病虫害生物防治工程技术研究中心、国家北方山区农业工程技术研究中心、河北农业大学植物保护学院、河北省农作物病虫害生物防治工程技术研究中心、国家北方山区农业工程技术研究中心、中国农业科学院研究生院 |
| 更多格式 | 高清、无水印(增值服务) |