《表2 海萝转录组测序整体情况》
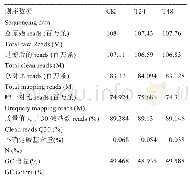
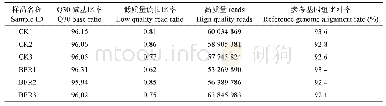
对海萝测序得到的clean reads进行过滤后发现,除T7-e外,所有样本的HQ quality clean reads占比均大于98%。将得到clean reads进行序列组装后,得到32 681条基因,N50为1 238 bp,平均GC含量为55.32%,组装得到的Unigenes平均长度为799 bp(表2),数据组装效果理想。将拼接获得的Unigenes进行功能注释后发现,共有12 813条Unigenes获得注释信息,19 868条基因暂无注释信息(表2)。利用BLASTX将Unigenes序列与Nr数据库进行比对后,确定其同源序列所属物种,统计比对到各个物种的同源序列数量发现(图2),海萝转录组组装得到的Unigenes其同源数目最多的物种是皱波角叉菜(Chondrus crispus),其次是另外一种可在极端环境中生存的红藻(Galdieria sulphuraria)。
| 图表编号 | XD0089704000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.05.15 |
| 作者 | 刘顺、胡自民、张全胜、段德麟 |
| 绘制单位 | 中国科学院海洋研究所海洋大科学研究中心实验海洋生物学重点实验室、青岛海洋科学与技术国家实验室海洋生物学与生物技术功能实验室、中国科学院大学、中国科学院海洋研究所海洋大科学研究中心实验海洋生物学重点实验室、青岛海洋科学与技术国家实验室海洋生物学与生物技术功能实验室、烟台大学海洋学院、中国科学院海洋研究所海洋大科学研究中心实验海洋生物学重点实验室、青岛海洋科学与技术国家实验室海洋生物学与生物技术功能实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式