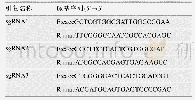
《表1 Etk sg RNA序列》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《Etk敲除及过表达细胞株构建并探讨Etk对细胞增殖的影响》
实验室利用CRISPR-Cas9技术进行基因敲除实验,成功建立了完整的实验流程[12,13]。在sg RNA设计网站chopchop(https://chopchop.cbu.uib.no/)输入Etk的基因信息,选择基因敲除功能。选取3条网站评分最高的针对Etk的sg RNA序列,序列见表1。在sg RNA序列两端分别加入BsmBⅠ的酶切位点产生粘性末端,将设计序列送至公司合成。将合成的双链sg RNA退火。55℃水浴情况下利用BsmBⅠ核酸限制酶酶切LentiCRISPR V2载体3小时产生与sg RNA相同的粘性末端;将退火产物与酶切后的载体混合,37℃利用T4 DNA连接酶反应1小时。将连接产物转化到感受态细胞Stbl3后培养在氨苄抗性的LB培养板中,培养12小时后挑取单克隆菌落进行基因测序。选取测序正确序列,菌液大摇提取质粒。
| 图表编号 | XD00171385200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.03.15 |
| 作者 | 苏宏、李钊、刘婷婷、陈超飞、王敏 |
| 绘制单位 | 中山大学附属第一医院转化医学中心、中山大学附属第一医院转化医学中心、中山大学附属第一医院转化医学中心、中山大学附属第一医院转化医学中心、中山大学附属第一医院转化医学中心 |
| 更多格式 | 高清、无水印(增值服务) |