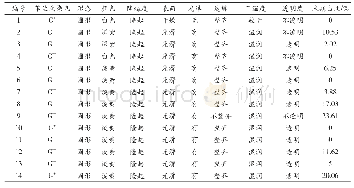
《表1 卵形鲳鲹基因组序列Contig和Scaffold组装统计结果》
采用SOAPdenovo 2.01对卵形鲳鲹测序基因组进行初步组装(K-mer=41),统计结果见表1。其中,Contig总长度为627.23 Mb,N50、N90分别为8.21和1.71 Mb,序列最大长度为95.96 Mb;Scalffold总长度为628.19 Mb,N50、N90分别为10.19和2.04 Mb,序列最大长度为126.91 Mb,基因组G+C含量为41.45%。选取500 bp以上的Contigs,根据其G+C分布及覆盖深度信息绘制散点图(图2),其中红色部分为散点图中点密度较大的部分。从图2右侧的Contig覆盖深度分布情况可看出,在Contig覆盖深度为47处为纯合峰,图中红色散点聚集区域是G+C的主要分布区域;图2上方的G+C含量主峰约出现在41%处,与计算得到的基因组G+C含量一致,且红色散点也分布在G+C含量为41%的附近。在Contig覆盖深度为70~110、G+C含量为30%~50%的区域和Contig覆盖深度为130~170、G+C含量为30%~50%的区域,出现小部分的G+C集中区域,推测这些区域为卵形鲳鲹基因组中的重复区域。
| 图表编号 | XD00156711600 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.05.01 |
| 作者 | 张永德、文露婷、罗洪林、林勇、杜雪松、余艳玲、韦孜娜、黄姻 |
| 绘制单位 | 广西水产科学研究院、广西水产遗传育种与健康养殖重点实验室、广西水产科学研究院、广西水产遗传育种与健康养殖重点实验室、广西水产科学研究院、广西水产遗传育种与健康养殖重点实验室、广西水产科学研究院、广西水产遗传育种与健康养殖重点实验室、广西水产科学研究院、广西水产遗传育种与健康养殖重点实验室、广西水产科学研究院、广西水产遗传育种与健康养殖重点实验室、广西水产科学研究院、广西水产遗传育种与健康养殖重点实验室、广西水产科学研究院、广西水产遗传育种与健康养殖重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式