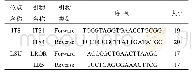
《表2 用于PCR扩增的cp DNA引物序列》
选取改良的CTAB法从干燥处理的山生柳嫩叶中提取基因组DNA(Porebski et al.,1997)。参照序列选取已上传到NCBI上的Salix arbutifolia、S.babylonica、S.interior、S.oreinoma、S.purpurea、S.suchowensis和S.tetrasperma等柳属植物叶绿体基因组序列,引物片段的选取参考之前的研究(Hamilton,1999;Scarcelli et al.,2011;Shaw et al.,2005),用软件Primer Premier 5.0(Singh et al.,1998)、BioXM 2.6(黄骥和张红生,2004)和SnapGene 3.2.1(McKeone et al.,2014)进行引物设计,共设计了21对引物用于PCR扩增。扩增反应体系为25μL:2.5μL的10×PCR Buffer(含1.5mmol·L-1MgCl2)、0.5μL的10 mmol·L-1dNTP、正反引物各0.5μL(10 pmol·L-1)、1个单位的Taq DNA酶(TaKaRa,大连)、15~50 ng的模板DNA,去离子水补齐到25μL。PCR反应扩增程序:94℃预变性3 min;94℃变性45 s;60℃退火45 s;72℃延伸30 s;35个循环;72℃延伸5 min;4℃保存。PCR反应产物送至生物工程(上海)股份有限公司测序。将获得21对引物在12个居群24个个体中进行PCR扩增预试验,筛选出获得两对遗传多态性较高的引物[5'trnG2G-3'trnG(UUC)和5'rpS12-rpL20]用于所有个体的扩增测序(表2)。
| 图表编号 | XD0088682900 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.09.01 |
| 作者 | 吴锦、杨茜、王久利、高庆波、张发起、陈世龙 |
| 绘制单位 | 中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、中国科学院大学、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、青海省作物分子育种重点实验室、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、青海省作物分子育种重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式