《表5 基于联合片段的山生柳分子变异分析》
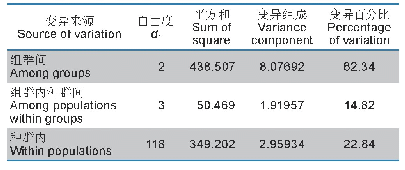
分子变异分析(AMOVA)结果表明,居群间遗传变异为6.30%,居群内遗传变异为93.70%(P<0.01),说明居群内遗传变异为山生柳遗传变异的主要来源(表5)。遗传分化系数FST=0.062 98,居群间遗传分化很小。根据基因流Nm与FST之间的关系(Kirk&Freeland,2011),Nm=(1-FST)/2FST,得到Nm为7.439,基因流很强。用PERMUT和DnaSP软件计算得出山生柳居群内平均遗传多样性(HS)为0.598(0.037 0)、总的遗传多样性(HT)为0.646(0.040 1)、居群间遗传分化GST=0.068,NST=0.075(NST>GST,P>0.05)。
| 图表编号 | XD0088682800 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.09.01 |
| 作者 | 吴锦、杨茜、王久利、高庆波、张发起、陈世龙 |
| 绘制单位 | 中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、中国科学院大学、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、青海省作物分子育种重点实验室、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、中国科学院高原生物适应与进化重点实验室中国科学院西北高原生物研究所、青海省作物分子育种重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式