《表1 中国大豆种质资源群体百粒重显著关联的SNPLDB标记位点》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《限制性两阶段多位点全基因组关联分析法在遗传育种中的应用》
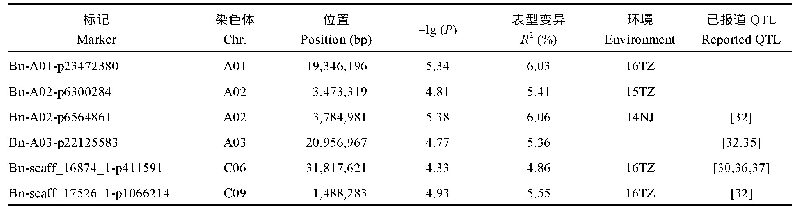
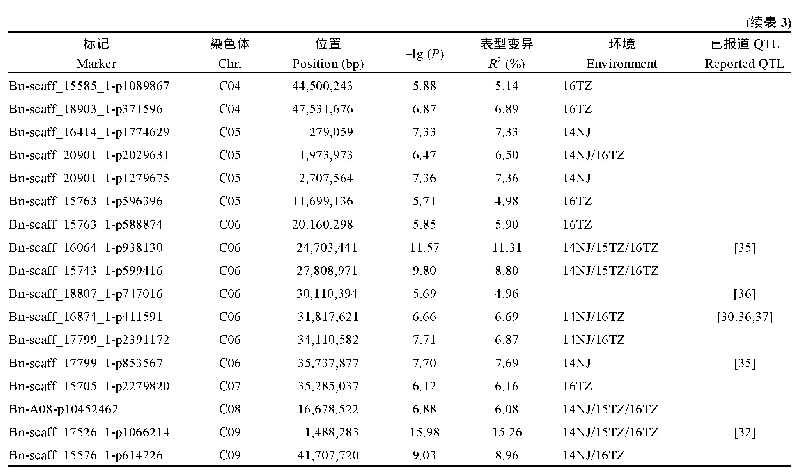
LC QTL:大贡献(R2≥1%)QTL;SC QTL:小贡献(R2<1%)QTL。...:省略了部分数据。a:Williams 82第一版参考基因组(Wm82.a1)LC QTL:Large(R2≥1%)contribution QTL;SC QTL:Small(R2<1%)contribution QTL.“...”:Data omitted.a:Williams 82 reference genome version 1(Wm82.a1
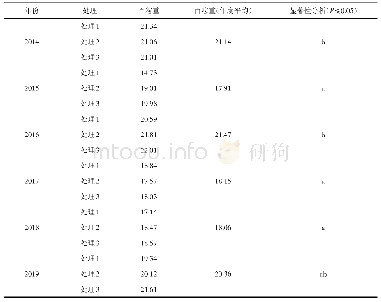
根据逐步回归方法的特点,除给出全模型显著的位点外,还可以给出每个入选位点的单独概率或显著性,通常和多重测验的校正概率相近,因而研究者还可根据需要采用特殊标准选取位点。例如,HE等[14]使用常规显著水平检测到139个大豆百粒重位点(表1),包括22个大效应(R2≥1%)位点和117个小效应(R2<1%)位点,总表型变异解释率分别为61.8%和36.4%。结果还包括了采用Bonferroni方法矫正显著水平检测的16个位点中的15个。因此,尽管没有必要对RTM-GWAS进行多重测验矫正,研究者仍然可以采用更严格的显著水平从常规显著水平下的结果中筛选个别显著程度高的大效应位点,而无需重新计算。例如,对于一个性状改良的育种方案,育种家可以使用0.05或0.01作为显著水平检测QTL,而对于候选基因克隆,研究者可以使用计算给出的单个位点的概率来筛选最重要的基因座位。
| 图表编号 | XD00180888300 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.05.01 |
| 作者 | 贺建波、刘方东、王吴彬、邢光南、管荣展、盖钧镒 |
| 绘制单位 | 南京农业大学大豆研究所、国家大豆改良中心、农业部大豆生物学与遗传育种重点实验室、作物遗传与种质创新国家重点实验室、江苏省现代作物生产协同创新中心、南京农业大学大豆研究所、国家大豆改良中心、农业部大豆生物学与遗传育种重点实验室、作物遗传与种质创新国家重点实验室、江苏省现代作物生产协同创新中心、南京农业大学大豆研究所、国家大豆改良中心、农业部大豆生物学与遗传育种重点实验室、作物遗传与种质创新国家重点实验室、江苏省现代作物生产协同创新中心、南京农业大学大豆研究所、国家大豆改良中心、农业部大豆生物学与遗传育种重点 |
| 更多格式 | 高清、无水印(增值服务) |