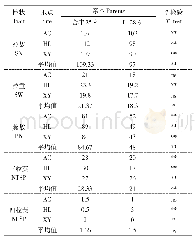
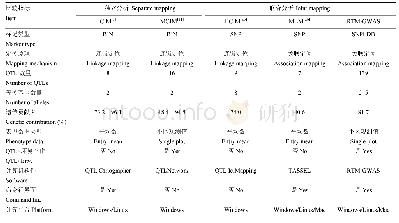
《表3 基于大豆NAM群体的五种QTL定位方法特点归纳比较》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《限制性两阶段多位点全基因组关联分析法在遗传育种中的应用》
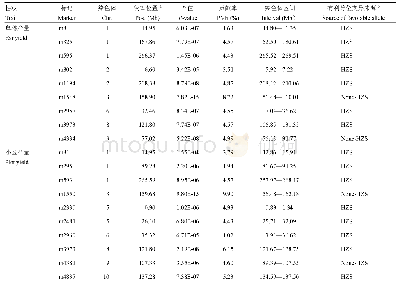
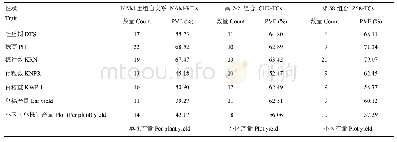
如前所述,尽管NAM群体通过一个共同亲本将多个RIL群体联系起来,提高了群体的遗传变异程度,然而以往分析方法却没将NAM群体作为一个统一完整群体。RTM-GWAS可通过构建SNPLDB标记对NAM群体进行统一分析。LI等[23]基于一个包含4个大豆RIL群体的NAM群体,比较了基于SNP标记的JICIM[6]和MLM方法,以及基于SNPLDB的RTM-GWAS方法(表3)。结果显示,3种方法分别检测到9、7和139个大豆开花期QTL,表型变异解释率分别是74.0%、40.6%和81.7%。该NAM群体有5个亲本,理论上位点上最多存在5个等位基因。而JICIM方法每个位点等位基因数目均为8,MLM方法每个位点等位基因数目均为2,显然不符合实际情况。RTM-GWAS方法每个位点等位基因数目最少2个,最多5个,合理地拟合了群体内的等位基因变异,更适用于NAM群体。
| 图表编号 | XD00180888200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.05.01 |
| 作者 | 贺建波、刘方东、王吴彬、邢光南、管荣展、盖钧镒 |
| 绘制单位 | 南京农业大学大豆研究所、国家大豆改良中心、农业部大豆生物学与遗传育种重点实验室、作物遗传与种质创新国家重点实验室、江苏省现代作物生产协同创新中心、南京农业大学大豆研究所、国家大豆改良中心、农业部大豆生物学与遗传育种重点实验室、作物遗传与种质创新国家重点实验室、江苏省现代作物生产协同创新中心、南京农业大学大豆研究所、国家大豆改良中心、农业部大豆生物学与遗传育种重点实验室、作物遗传与种质创新国家重点实验室、江苏省现代作物生产协同创新中心、南京农业大学大豆研究所、国家大豆改良中心、农业部大豆生物学与遗传育种重点 |
| 更多格式 | 高清、无水印(增值服务) |