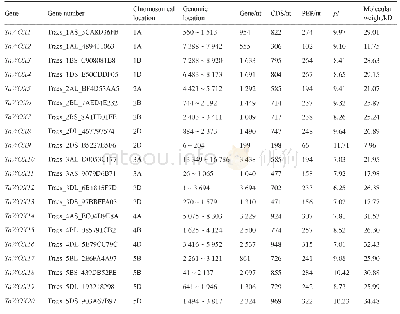
《表1 玉米AMT基因及蛋白信息》
首先利用Bio Edit软件建立玉米全蛋白序列数据的本地数据库;然后利用pfam数据库(http://pfam.janelia.org/search/sequence)中的隐马尔可夫模型(HMM)将其与拟南芥AMT结构域的氨基酸序列进行BLAST序列比对,初步筛选出候选基因序列;再进行Pfam分析验证其蛋白是否含有保守的AMT结构域,并去除不含有保守的AMT结构域的基因序列;最后利用Clustal W方法对候选AMT基因蛋白序列进行多序列比对,去掉候选基因中的重复序列,即得到预测的AMT基因。为确保预测结果准确性,本实验对每个蛋白基因的ORF序列在NCBI网站进行BLAST搜索及本地同源性分析,去除部分不可靠序列,预测出候选AMT基因,最终得到8个含有AMT结构的基因,各基因的位置将其分别命名为Zm AMT-1,Zm AMT-2,Zm AMT-3,Zm AMT-4,Zm AMT-5,Zm AMT-6,Zm AMT-7,Zm AMT-8。从获得的8个铵转运蛋白信息知,玉米自交系B73铵转运蛋白的氨基酸残基数目为460~500,等电点(PI)介于6.50~8.20,大多数接近中性或偏碱性。具体如表1所示。
| 图表编号 | XD00187483100 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2018.03.15 |
| 作者 | 李红梅、韩国民 |
| 绘制单位 | 安徽新华学院信息工程学院、安徽农业大学生命科学学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式