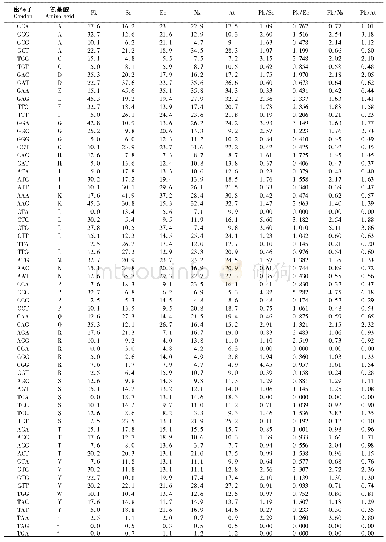
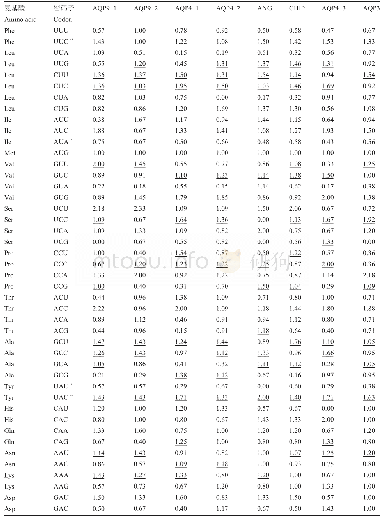
《表2 EgAQPs基因密码子选用偏好性参数》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《细粒棘球绦虫水通道蛋白基因家族成员密码子偏好性分析》
注:T3s,C3s,A3s,G3s,GC3s分别表示密码子的第3位是T,C,A,G,G+C的含量
有效密码子数(effective number of codons,ENC)的参考范围为20~61,越靠近20偏好性越强。CodonW软件分析可以发现EgAQPs基因的ENc值为57.66,说明EgAQPs基因各密码子使用偏离随机选择的程度比较一致(表2)。密码子适应指数(codon adaptation index,CAI)值在0~1之间,值越接近1,基因的密码子偏好性越强,EgAQPs基因CAI平均值为0.22。密码子偏好指数(codon bias index,CBI)往往用来阐释某一特定的基因中所有最优密码子的组分情况,EgAQPs基因CBI平均为0.08,以上结果均说明E-gAQPs基因具有较弱的密码子偏好性。EgAQPs基因G3s平均含量为26.44%,C3s平均含量为37.66%,均高于A3s及T3s的含量。GC含量的平均值为50.33%,GC3s含量的平均值为53.26%,两值均大于50%,这表明EgAQPs基因的CDS编码区碱基选择及其密码子第三位的碱基选择上均存在较弱的C/G的偏好性,偏好使用以C/G结尾的密码子。
| 图表编号 | XD00147633600 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.06.25 |
| 作者 | 范俊杰、吴宏烨、李锴、叶彬 |
| 绘制单位 | 重庆医科大学病原生物学教研室、重庆医科大学病原生物学教研室、重庆医科大学病原生物学教研室、重庆医科大学病原生物学教研室、重庆医科大学分子医学与肿瘤研究中心 |
| 更多格式 | 高清、无水印(增值服务) |