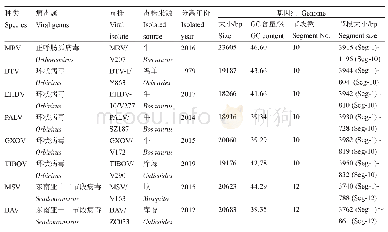
《表3 本研究使用毒株NGS测序数据统计》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《通过全长cDNA扩增及高通量测序技术获取呼肠孤病毒科病毒的全基因组序列》
-:尚未公布病毒基因组序列;病毒种类及病毒属全称参见表1
对7种呼肠孤病毒科病毒的NGS测序结果显示,不同毒株全基因组PCR扩增产物测序产生的数据量在1.3~1.9 G,获取的原始reads数在393 577800~571 343 600;过滤除去低质量的reads,用于病毒基因组拼接的reads (Q>30)数量在293 016 800~423 210 600,98.34%~99.91%过滤后reads被用于病毒基因组de novo组装,每个碱基位点的测序深度在6 000~20 000次,组装获取的病毒基因组大小在18266~23 605 bp,基因组GC含量在39.29%~46.60%,不同病毒的基因组节段数目在10~12,节段大小在788 bp (Seg-12)~3 982 bp (Seg-1)(表1,表3)。
| 图表编号 | XD00204540800 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2021.01.25 |
| 作者 | 李占鸿、宋子昂、朱建波、杨振兴、李卓然、李华春、杨恒 |
| 绘制单位 | 云南省畜牧兽医科学院云南省热带亚热带动物病毒重点实验室、云南农业大学动物医学院、云南省畜牧兽医科学院云南省热带亚热带动物病毒重点实验室、云南省畜牧兽医科学院云南省热带亚热带动物病毒重点实验室、云南省畜牧兽医科学院云南省热带亚热带动物病毒重点实验室、云南省畜牧兽医科学院云南省热带亚热带动物病毒重点实验室、云南省畜牧兽医科学院云南省热带亚热带动物病毒重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |