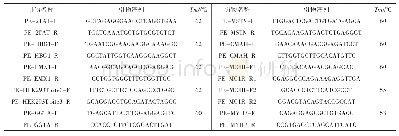
《表4 接头序列和引物的碱基序列》
将从测序仪上扩增得到的原始数据24个样品、8对引物组合扩增产物利用GeneMarker 2.2软件进行生物信息学分析,通过比较各泳道内分子量内标的位置与各样品峰值的位置后,可以获得大小不等的扩增片段信息。再根据条带的有无转化为0、1数据矩阵。通过对引物多态性的百分率与多态性信息指数(PIC)的计算,PIC=Σ(1-Pi2)/n,其中,Pi为任一引物组合第i条多态性带在所有供试材料中出现的频率;n为供试材料的总数。利用Popgene和NTSYS软件对样品进行遗传多样性分析。利用POPGENE32计算各个居群的多态位点百分比(PPL);遗传多样性指数(Nei's);Shannon's指数(I)等;采用NTSYSpc 2.11软件进行UPGMA聚类分析;PCA主成分分析。
| 图表编号 | XD00152975500 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.08.14 |
| 作者 | 杨成龙、周明强、班秀文、李志芳、黎青、刘凡值 |
| 绘制单位 | 贵州省农业科学院亚热带作物研究所、贵州省农业科学院亚热带作物研究所、贵州省农业科学院亚热带作物研究所、贵州省农业科学院亚热带作物研究所、贵州省农业科学院亚热带作物研究所、贵州省农业科学院亚热带作物研究所 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式