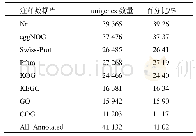
《表2 不同数据库中江鳕转录组unigenes注释统计》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《基于RNA-seq技术的江鳕不同组织转录组比较分析》
≥300 nt:注释到该数据库的长度大于300个碱基的unigenes数;≥1000 nt:注释到该数据库的长度大于1000个碱基的Unigenes数;COG:蛋白相邻类的聚簇数据库;GO:基因本体数据库;KEGG:京都基因与基因组百科全书;KOG:真核生物蛋白质同源簇数据库;Pfam:蛋白质家族的集合数据
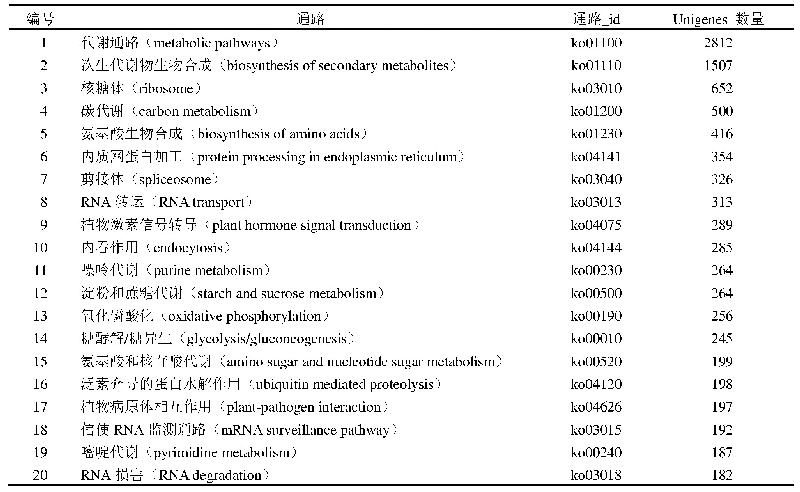
通过BLAST 2.0和HMMER 3.1软件与相应数据库比对,最终获得有注释信息的unigenes数量为32 745个,约占总unigenes数量的30.87%(表2),比对到NR数据库的unigenes数量最多,为32 122条,COG注释的信息最少,仅为7 203条。unigenes在7个不同数据库中的同源比对数目占总unigenes的百分比分别为6.79%(COG)、10.23%(GO)、13.04%(KEGG)、20.42%(KOG)、21.05%(Pfam)、17.47%(Swiss-Prot)、30.28%(NR)。这些获得注释的基因为进一步研究基因功能提供了参考。
| 图表编号 | XD00121578900 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.02.25 |
| 作者 | 杨天燕、蒋艳琳、韩志强、孟玮 |
| 绘制单位 | 浙江海洋大学水产学院、浙江海洋大学水产学院、浙江海洋大学水产学院、浙江省海洋水产研究所、浙江省海洋渔业资源可持续利用技术研究重点实验室、农业部重点渔场渔业资源科学观测实验站 |
| 更多格式 | 高清、无水印(增值服务) |