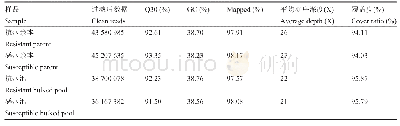
《表2 各样品SLAF-seq测序数据统计表》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《基于SLAF-seq技术分析甜、糯玉米种质遗传多样性》
通过电子酶切预测,最终选用RsaI进行酶切,将酶切片段长度为364~394 bp的序列定义为SLAF标签,预测能得到155 447个SLAF标签,在玉米基因组10个染色体上分布基本均匀,平均SLAF间距在14 497~15 017 bp。序列分析表明,实验中RsaI的酶切效率为94.26%,共得到209.00 MReads。通过SOAP[15]软件将Control的测序reads与其参考基因组进行比对,结果显示,双端比对效率在97.52%,比对效率基本正常,SLAF建库正常,说明SLAF标签酶切方案可行。对各样品的测序数据进行统计,共获得209.38 MReads数据,测序平均Q30(测序质量值大于或等于30的碱基所占百分比)为91.04%,表明测序质量很高,平均GC含量为44.05%(表2)。
| 图表编号 | XD0080772200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.08.15 |
| 作者 | 李余良、索海翠、韩福光、刘建华、胡建广、高磊、李武 |
| 绘制单位 | 广东省农业科学院作物研究所、广东省遗传改良重点实验室、广东省农业科学院作物研究所、广东省遗传改良重点实验室、广东省农业科学院作物研究所、广东省农业科学院作物研究所、广东省农业科学院作物研究所、广东省遗传改良重点实验室、广东省农业科学院作物研究所、广东省遗传改良重点实验室、广东省农业科学院作物研究所、广东省遗传改良重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |