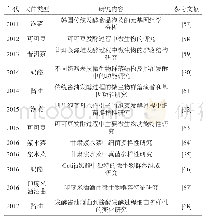
《表5 2015年以来基于宏基因组文库的生物信息学方法筛选得到的生物催化剂》
采用这种方法,检索得到7篇文献(表5),提示这种方法是一种有前途的筛选方法,但这种方法需要构建宏基因组文库.这种方法没有建立一种统一标准的操作流程,不同研究者在各自具体情况下借助不同的生物信息学方法得到特定的生物催化剂.以Tan等人鉴定植酸酶为例,他们采用主要的生物信息学和实验鉴定流程如下:首先从18个公共资源上获得的宏基因组数据中搜索得到11个推断的HAP肌醇六磷酸酶基因,然后在大肠杆菌中进行过表达,从而筛选得到高活性的植酸酶,最后通过实验证实了他们的结论[67].
| 图表编号 | XD0061509000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.04.25 |
| 作者 | 彭司华、孙丹、袁文亮、卫偲 |
| 绘制单位 | 上海海洋大学水产与生命学院发育生物学系、水产种质资源发掘与利用教育部重点实验室(上海海洋大学)、农业部国家水生动物病原库(上海海洋大学)、科学技术部海洋生物科学国际联合研究中心(上海海洋大学)、上海海洋大学水产与生命学院发育生物学系、水产种质资源发掘与利用教育部重点实验室(上海海洋大学)、农业部国家水生动物病原库(上海海洋大学)、科学技术部海洋生物科学国际联合研究中心(上海海洋大学)、上海理工大学光电信息与计算机工程学院、上海海洋大学水产与生命学院发育生物学系、水产种质资源发掘与利用教育部重点实验室(上海 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式