《表3 NGSengine和HLAminer的分型结果分辨率及与Illumina分型结果一致性统计》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《三代测序与靶向捕获技术联用进行高分辨HLA基因分型及MHC区域单倍体型精细鉴定》
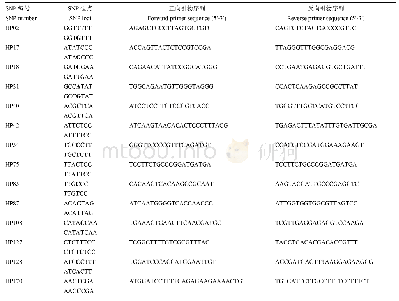
114个基因中有99个完全一致,15个不一致,分型结果体现在第8位分型结果的差异,这类差异可通过软件优化与参数调整进一步减少。
首先,HLAminer软件三代与二代数据的分型结果间存在差异,而NGSengine软件三代与二代数据的分型结果保持一致(表3)。此外,当subreads的数据量足够时,基于subreads数据的分型结果与CCS数据基本一致,但前者往往会多出一个代表错配信息的后缀。以HCC5样本的DRB5基因为例,其基于subreads的分型结果为DRB5*02:023,而CCS对应的分型结果为DRB5*02:02,这表明subreads的结果在外显子区域存在3个错配碱基。从单碱基准确性角度考虑,使用CCS数据对HLA基因分型应该是更好的选择。
| 图表编号 | XD0045287200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.04.01 |
| 作者 | 陈佳、舒明月、里进、付爱思、杨帆、王邹、李一荣、邓子新、刘天罡 |
| 绘制单位 | 武汉大学药学院组合生物合成与新药发现教育部重点实验室、武汉大学药学院组合生物合成与新药发现教育部重点实验室、武汉大学中南医院检验医学中心、武汉大学药学院组合生物合成与新药发现教育部重点实验室、武汉生物技术研究院公共技术服务平台、武汉生物技术研究院公共技术服务平台、武汉大学中南医院检验医学中心、武汉大学药学院组合生物合成与新药发现教育部重点实验室、武汉大学药学院组合生物合成与新药发现教育部重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |