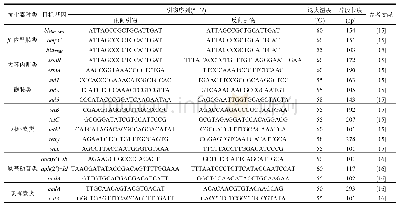
《表4 引物A145F与目标和非目标片段错配位点Table 4 Mismatch sites between A145F primer with target fragments and non ta
18sr DNA是较早被用于真核藻类分子鉴定的基因,其特点是序列高度保守、进化速率缓慢,所以它的变异程度不高,分辨力相对较弱[13];这就需要在设计引物时选择目标扩增类群的同源性区域且该区域内存在与非目标扩增类群错配位点。引物A145F/Dia516R与非目标扩增类群中的红藻存在至少3个位点的错配,与金藻、绿藻等非目标扩增类群错配位点相对较少;所以该引物的克隆文库测序结果存在上述四类非目标扩增类群,其中绿藻和细菌、真菌、原生动物等微生物所占比例最大;此外,引物A145F/Dia516R与异极藻、直链藻、菱形藻、小环藻、海链藻五类目标扩增类群存在有1~2个位点错配,却检出直链藻与海链藻,其原因可能是引物对这两类硅藻DNA具有一定的偏好性(表4~5)。硅藻通用引物18s F/18sR与十三类硅藻扩增类群和金藻、绿藻、红藻、艾美虫、丝足虫等非目标扩增类群均无错配位点,其硅藻检出率相对较低,主要原因是特异性不足。
| 图表编号 | XD0018702800 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2018.06.20 |
| 作者 | 胡蝶、程宝文、邢豫明、皮之云 |
| 绘制单位 | 昆明医科大学法医学院、昆明医科大学法医学院、云南省公安厅、昆明医科大学法医学院、云南省公安厅、昆明医科大学法医学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式