《表1 甘薯编码NBS-LRR蛋白的基因数量及其分类》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《甘薯基因组NBS-LRR类抗病家族基因挖掘与分析》
a:数据来源于[42];b:数据来源于[43];c:数据来源于[44];d:数据来源于[45]。
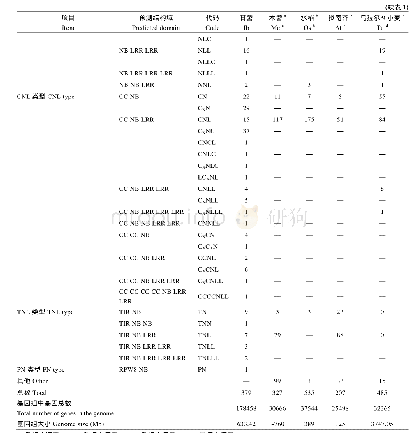
采用snap程序对甘薯全基因组序列进行CDS区识别预测,得到甘薯15条染色体CDS序列178,458个。利用hmmsearch程序筛选甘薯基因组中含有NB-ARC结构域的序列,以E-value≤0.01为标准,获得相关蛋白序列432个。从中选取高特异蛋白质序列(E-value≤1E-60)构建甘薯特异的NB-ARC HMM模型,利用甘薯特异的HMM模型再次预测甘薯全基因组序列的NB-ARC保守结构域,获得甘薯含有NB-ARC结构域的特异蛋白序列735个(E-value≤0.01)。去除氨基酸长度小于200以及结构域缺失严重的序列,最终得到379个甘薯NBS-LRR家族基因,占甘薯全基因组基因数目(178,458)的0.212%。根据TIR/RPW8/LRR结构域和CC结构域分为N(NBS)、NL(NBS-LRR)、CNL(CC-NBS-LRR)、TNL(TIL-NBS-LRR)和PN(RPW8-NBS)4个亚家族类型(表1),其中N型120个,NL型103个,CNL型133个,TNL型22个,PN型1个。分析发现,NBS/LRR结构域重复数和位置存在差异,在序列结构域读取文件中含有RX-CC_like结构域,此结构域为马铃薯抗X病毒和类似蛋白的Coiled-coil结构域(Coiled coil domain of the potato virus X resistance protein and similar proteins)[40],记为Cx结构域,以区分Pepcoil程序得到的CC结构域。因此,根据NBS/LRR结构域重复数和位置差异、CC结构域类型进一步分为34个小类(表1)。
| 图表编号 | XD00174478600 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.08.12 |
| 作者 | 黄小芳、毕楚韵、石媛媛、胡韵卓、周丽香、梁才晓、黄碧芳、许明、林世强、陈选阳 |
| 绘制单位 | 福建农林大学作物生物技术福建省高校重点实验室、福建农林大学农学院、福建农林大学作物生物技术福建省高校重点实验室、福建农林大学农学院、福建农林大学农学院、福建农林大学植物保护学院、福建农林大学生命科学学院、福建农林大学生命科学学院、福建农林大学生命科学学院、福建农林大学作物生物技术福建省高校重点实验室、福建农林大学农学院、福建农林大学作物生物技术福建省高校重点实验室、福建农林大学生命科学学院、福建农林大学作物生物技术福建省高校重点实验室、福建农林大学农学院、福建农林大学教育部作物遗传育种与综合利用重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |