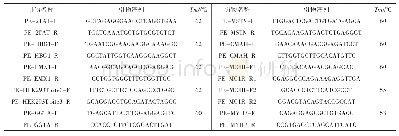
《表4 转化不同靶序列编辑效率统计结果》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《基于优化sgRNA系统提高海岛棉CRISPR/Cas9基因组编辑功效的研究》
表格中分子代表突变个数,分母代表克隆测序个数;概率值均为平均值。
将转化Gb U6-5P-GGB-sgRNA1和转化Gb U6-5P::GGB-sgRNA1-Gb U6-4P::ERA1-sgRNA2提取的基因组DNA采用酶切(Kpn I、Sac I)后PCR方式检测,转化Gb U6-5P::GGB-sgRNA1-Gb U6-4P::GGB-sgRNA2采用直接PCR方式检测,结果如图5,转化Cas9 I型靶序列编辑载体的原生质体DNA酶切后PCR检测存在扩增条带,对照则未出现明显条带,初步证明,转化Gb U6-5P-GGB-sgRNA1和转化Gb U6-5P::GGB-sgRNA1-Gb U6-4P::ERA1-sgRNA2编辑载体造成海岛棉基因组相应的靶位点突变,将上述PCR产物克隆后测序结果(图6和图7)分析发现,所有转化靶序列的原生质体均检测到碱基突变现象,转化与之对应空载体的原生质体未检测到碱基突变现象,对比转化不同载体的原生质体,虽然靶序列作用位点相同,但引发碱基突变的个数和位置均不同。分析后认为,可能是转化不同编辑载体引起不同程度编辑效应造成的结果。针对转化Shift相关靶序列的基因组编辑载体,也获得与上述相同的实验结果,相比同一位点2种(No shift sgRNA和shift sgRNA)不同靶序列类型,转化No Shift靶序列的原生质体其编辑效率高于转化Shift靶序列,增幅为20.0%~49.6%(表4)。转化Cas9II型编辑载体结果与上述类似。
| 图表编号 | XD0096084000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.10.12 |
| 作者 | 李继洋、胡燕、姚瑞、代培红、刘晓东 |
| 绘制单位 | 新疆农业大学农学院、新疆农业大学农业生物技术重点实验室、石河子大学生命科学院、新疆农业大学农学院、新疆农业大学农业生物技术重点实验室、石河子大学生命科学院、新疆农业大学农学院、新疆农业大学农业生物技术重点实验室、新疆农业大学农学院、新疆农业大学农业生物技术重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |