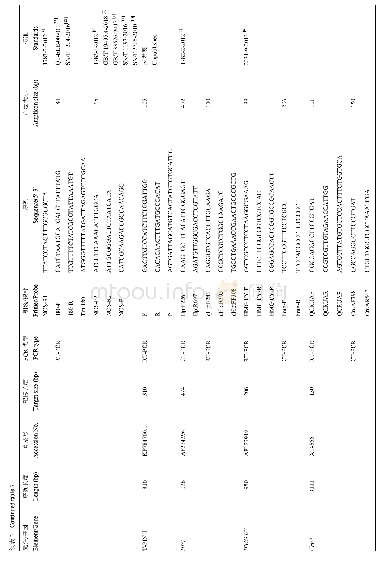
《表3 sgRNA1和sgRNA2脱靶位点的核苷酸序列》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《应用CRISPR/Cas9和Cas9-D10A建立Nsun5基因敲除小鼠模型并分析脱靶效应》
PAM序列显示为绿色。碱基错配显示为红色。
为了检测这两种策略得到的基因敲除首建鼠是否存在脱靶效应,选取由Cas9/sgRNA和Cas9-D10A/sgRNA构建的Nsun5基因敲除首建鼠各3只(Cas9:5号、7号、12号;Cas9-D10A:1号、2号、6号),分析并对比Cas9和Cas9-D10A得到首建鼠的脱靶效应。首先针对两个sgRNA各预测了10个最容易发生脱靶效应的位点(表3),然后设计引物进行PCR扩增,之后进行T7EN1酶切检测脱靶效应(图2)。从图中可以看出,和对照相比,选取的6只小鼠针对sgRNA1和sgRNA2潜在的20个脱靶位点均无突变,对T7EN1酶切有切割条带的PCR产物,进行了T-A克隆测序验证,发现对应的PCR产物存在单核苷酸多态性或由重复序列导致的Taq酶扩增错误。
| 图表编号 | XD00224215200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.09.15 |
| 作者 | 王仿竹、陈红全、王建瑛、沈彬 |
| 绘制单位 | 南京医科大学生殖医学国家重点实验室、浙江大学医学院附属邵逸夫医院检验科、南京医科大学生殖医学国家重点实验室、南京医科大学生殖医学国家重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |