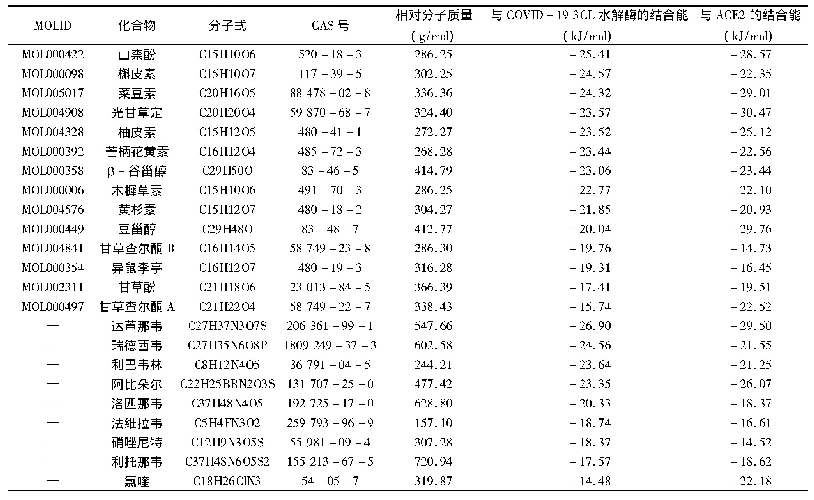
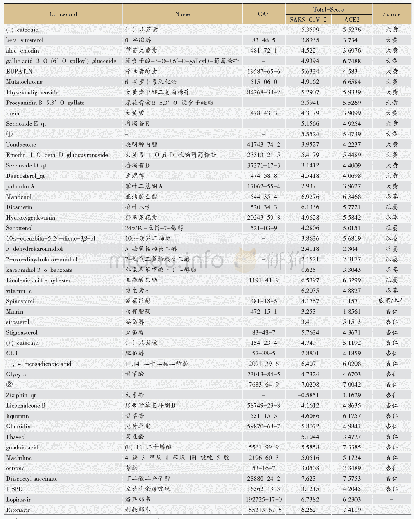
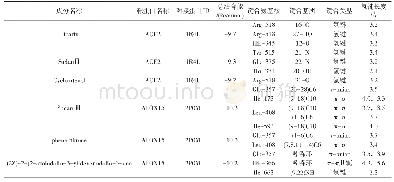
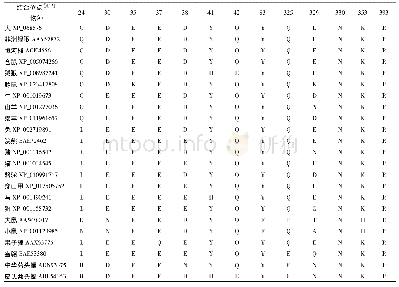
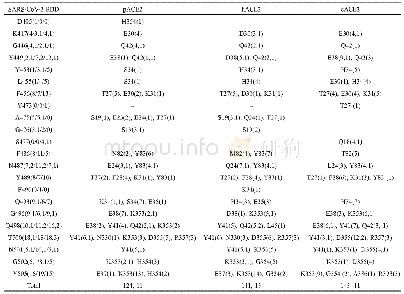
《表2 SARS-Co V-2 RBD结合p ACE2、h ACE2和c ACE2的结构比较a)》
a) SARS-CoV-2 RBD氨基酸括号内的数字表示与pACE2(前者)、hACE2(中间)和cACE2(后者)形成的范德华力和氢键相互作用数量.ACE2氨基酸括号中的数字表示与SARS-CoV-2 RBD形成的范德华力和氢键相互作用数量.逗号后的数字表示形成的氢键相互作用数量.上述分析的范德华力距离为4以内,
进一步比较3个复合物结构的相互作用细节发现,除D405和F490外,SARS-Co V-2 RBD与p ACE2相互作用的其余氨基酸均与h ACE2相同(表1).D405与p ACE2的H354形成1个相互作用,而与h ACE2没有相互作用;F490与h ACE2形成1个相互作用,而与p ACE2没有相互作用.与结合c ACE2相比,SARS-Co V-2 RBD与p ACE2相互作用的氨基酸有5个不同,分别为D405、Y473、A475、G476和S477 (表2),D405同样与c ACE2也没有相互作用,而与p ACE2形成1个相互作用;Y473与c ACE2形成1个相互作用,S477与c ACE2形成氢键,而二者与p ACE2没有相互作用;A475和G476与p ACE2分别形成偶极相互作用和氢键,而与c ACE2没有相互作用.虽然SARS-Co V-2 RBD与p ACE2、h ACE2和c ACE2相互作用的氨基酸略有不同,但参与相互作用的氨基酸总数是相近的,分别为19、19和18.SARS-Co V-2 RBD与p ACE2、h ACE2和c ACE2相互作用界面的面积分别为913.8、876.8和960.2?2,虽然其与h ACE2相互作用界面的面积最小,但是二者之间的范德华力和氢键相互作用略多于p ACE2和c ACE2(分别为124、141和143、11、13和11)(表2).值得注意的是,由于SARS-Co V-2 RBD的K417与p ACE2的E30距离变远,失去了氢键相互作用,进而导致其与p ACE2的E30相互作用弱于h ACE2的D30和c ACE2的E30(表2).这些结果提示SARS-Co V-2 RBD与p ACE2的作用力低于h ACE2,这与SPR结果相符.通过比较SARS-Co V-2 RBD结合p ACE2、h ACE2和c ACE2的足迹,发现参与相互作用的大部分氨基酸在3种ACE2s中是保守的,而p ACE2和h ACE2仅有1个氨基酸不同(图3(e),(f)),p ACE2和c ACE2有7个氨基酸的差异(图3(e),(g)).这些结果表明,相比于SARS-Co V-2 RBD-c ACE2复合物结构,SARS-Co V-2 RBD-p ACE2更相似于SARS-Co V-2 RBD-hACE2.
| 图表编号 | XD00200896300 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2021.01.10 |
| 作者 | 仵丽丽、苏佳岐、牛胜、陈茜、张艳芳、严景华、施一、齐建勋、高福、王奇慧 |
| 绘制单位 | 中国科学院微生物研究所微生物生理与代谢工程重点实验室、中国科学院大学、中国科学院微生物研究所病原微生物与免疫学重点实验室、中国科学院微生物研究所病原微生物与免疫学重点实验室、山西农业大学动物科技学院、中国科学院微生物研究所病原微生物与免疫学重点实验室、安徽大学物理科学与信息学院、中国科学院微生物研究所病原微生物与免疫学重点实验室、中国科学院微生物研究所微生物生理与代谢工程重点实验室、中国科学院微生物研究所病原微生物与免疫学重点实验室、中国科学院微生物研究所病原微生物与免疫学重点实验室、中国科学院微生物研究 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式