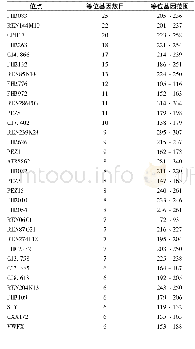
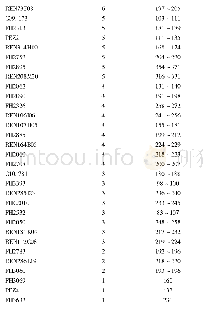
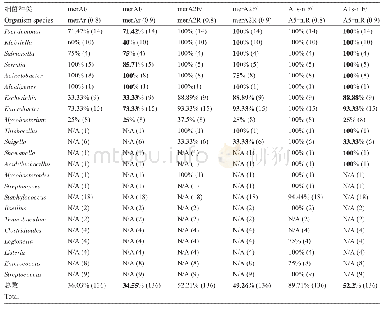
《表2 SPCR预测每对引物能够检测到的包含merA基因的细菌种类及数目》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《细菌汞抗性基因merA特异性的3对PCR引物的检测范围的比较》
注:N/A:根据SPCR预测,引物对没有检测到属于相应细菌的merA基因序列;后面括号内的数字代表总序列;(0.8):产物扩增系数为0.8,原文献推荐值;(0.9):产物扩增系数为0.9,相当于更严谨的PCR条件下;字体加粗:在扩增系数为0.9时,每对引物扩增的序列数占相应细菌总序列数的比例
从NCBI的RefSeq参考序列数据库中(https://www.ncbi.nlm.nih.gov/refseq/)下载了118条merA基因序列,与在UniProtKB数据库的Swiss-Prot库中以及BacMet库中下载的所有经过实验验证的18条merA基因序列合并,去除冗余序列,得到共计136条(23个属)非冗余merA基因序列。将这136条序列作为模板,导入SPCR程序中(Cao et al.,2005),模拟预测merA2F/merA2R,merAf/merAr和A1s-n.F/A5-n.R3对引物分别能够检测的merA基因的数目及细菌种类(表2)。
| 图表编号 | XD00196498000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.10.25 |
| 作者 | 陈秋蓉、王凌华、赵立平、申剑 |
| 绘制单位 | 上海交通大学系统生物医学研究院,系统生物医学教育部重点实验室、上海交通大学生命科学技术学院,微生物代谢国家重点实验室、上海交通大学生命科学技术学院,微生物代谢国家重点实验室、上海交通大学系统生物医学研究院,系统生物医学教育部重点实验室、上海交通大学生命科学技术学院,微生物代谢国家重点实验室、上海交通大学系统生物医学研究院,系统生物医学教育部重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |