《表3 两个蛋白质互作用网络》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《基于XGBoost与拓扑结构信息的蛋白质复合物识别算法》
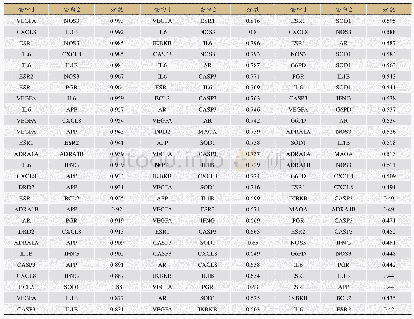
本文将XGBP算法与目前较为经典的八种算法,包括MCODE、MCL、CMC、HC-PIN、COACH、ClusterONE、DCU以及WCOACH在DIP[18]和Krogan[19]两个酵母菌相互作用网络相比较(见表3所示)。蛋白质复合物标准库采用了CYC2008[20]和MIPS标准库,两个标准库分别由408个复合物和428个复合物所组成。
| 图表编号 | XD00163185900 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.05.10 |
| 作者 | 徐周波、杨健、刘华东、黄文文 |
| 绘制单位 | 广西可信软件重点实验室(桂林电子科技大学)、广西可信软件重点实验室(桂林电子科技大学)、广西可信软件重点实验室(桂林电子科技大学)、桂林电子科技大学机电工程学院、广西可信软件重点实验室(桂林电子科技大学) |
| 更多格式 | 高清、无水印(增值服务) |


![表3[φ]取值:基于符号图卷积网络的药物互作用关系预测](http://bookimg.mtoou.info/tubiao/gif/XDJS202016003_09600.gif)