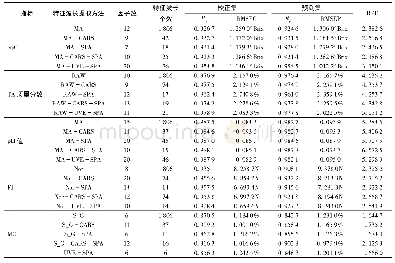
《表1 基于原始及预处理全光谱建立的PLSR模型性能》
为在掺假样品中定量分析大豆蛋白含量,随机选取96个样品加入训练集(16梯度×6样品),剩余32个样品作为预测集(16梯度×2样品),针对3种不同大豆蛋白分别建立基于原始及预处理光谱的PLSR模型,每个模型均采用留一法进行交叉验证,所有建模结果如表1所示。通过比较不同的预处理方法,总体上无论掺入何种大豆蛋白种类,全光谱的预测精度均令人满意,可以达到R2≥0.98,均方根误差在1.41%以内。3种大豆蛋白预测性能的横向比较发现,SPC的预测效果最好,原始光谱的模型预测精度可达Rp2=0.998 4,预测集均方根误差为0.37%且预测与偏差之比(Ratio of prediction to deviation,RPD)[18]为23.89。对于SPF,二阶导数预处理后的全光谱模型性能最优,Rp2=0.991 6,预测集均方根误差为0.81%且RPD为10.91,而SPI的预测模型中,不采用预处理的全光谱建立的模型可达Rp2=0.983 7,预测集均方根误差为1.16%且RPD为7.62。
| 图表编号 | XD00121679000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.12.25 |
| 作者 | 王伟、姜洪喆、贾贝贝、鹿瑶 |
| 绘制单位 | 中国农业大学工学院、中国农业大学现代农业装备优化设计北京市重点实验室、南京林业大学机械电子工程学院、中国农业大学工学院、中国农业大学现代农业装备优化设计北京市重点实验室、中国农业大学工学院、中国农业大学现代农业装备优化设计北京市重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式