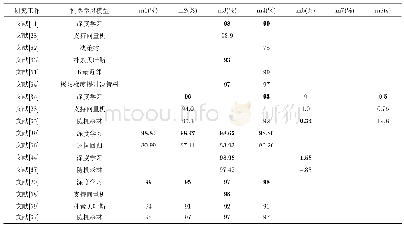
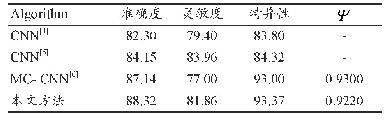
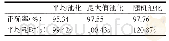《表1 基于深度学习的正常组织勾画方法及结果对比》
DSC:戴斯相似系数(dice similarity coefficient,DSC);ASD1:平均对称表面距离(average symmetric surface distance,ASD);RVD:相对体积差异(relative volume difference,RVD)数据库:(1)MICCAI-SLiver07:2007医学图像计算和计算机辅助干预国际会议-肝脏分割挑战数据库(S
放疗计划设计时,首先在CT或MRI图像进行正常组织和肿瘤靶区的勾画,对于靶区周围的正常组织器官,不同器官有不同的耐受剂量,在一定程度上决定了放疗处方剂量水平。精确迅速地分割正常组织,是实现放疗计划自动设计的第一步,分割结果直接影响放疗计划设计、评估的准确性。如表1所示,列出了近几年深度学习方法在正常组织自动勾画中的应用,并对分割方法和结果进行了比较。
| 图表编号 | XD00106173000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.10.25 |
| 作者 | 张珺倩、张远、尹勇、朱健、李宝生 |
| 绘制单位 | 济南大学信息科学与工程学院、济南大学信息科学与工程学院、山东大学附属山东省肿瘤医院放射肿瘤科、山东大学附属山东省肿瘤医院放射物理技术科、山东大学附属山东省肿瘤医院放射肿瘤科、山东大学附属山东省肿瘤医院放射物理技术科、山东大学附属山东省肿瘤医院放射肿瘤科、山东大学附属山东省肿瘤医院放射物理技术科 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式