《表2 不同性能在3种全基因组数据分析工具间的比较》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《全基因组数据分析工具TB Profiler v2.8.0、Mykrobe v0.7.0和PhyResSE v1.0在耐药结核病检测中的价值》
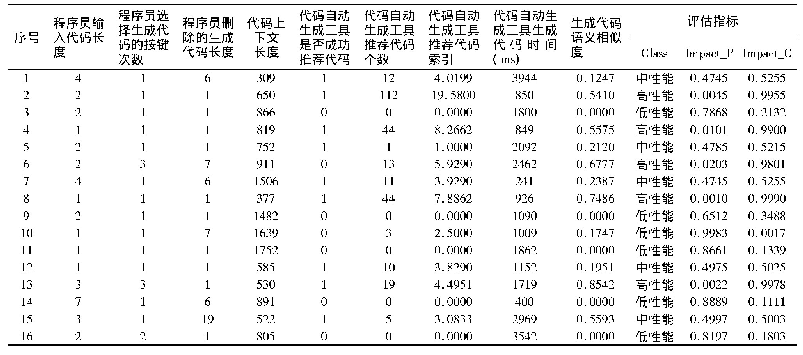
TB Profiler、Mykrobe和PhyResSE操作简单,给出的耐药检测结果简单易懂,并且给出了菌株家系信息(表2)。在处理时间方面,一个100倍测序深度的样本(约450兆)使用网页版TB Profiler和PhyResSE从上传完成到得到耐药结果需要约90min,而使用软件版Mykrobe则速度较快,只需要约30min。在批量操作方面,PhyResSE网页版提供批量上传,TB Profiler和Mykrobe只能在命令行版本批量分析数据。此外,TB Profiler和Mykrobe可以根据用户个性化需求修改使用的突变数据库,从而纳入新发现的耐药突变,不断提高检测的准确性。TB Profiler在命令行版本中通过编辑源代码来修改突变数据库,Mykrobe在命令行版本中通过使用Python代码生成器进行调整。
| 图表编号 | XD00200927000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.11.10 |
| 作者 | 李冰莹、郑旭彬、胡屹、徐飚 |
| 绘制单位 | 复旦大学公共卫生学院流行病学教研室国家卫生健康委员会卫生技术评估重点实验室、复旦大学公共卫生学院流行病学教研室国家卫生健康委员会卫生技术评估重点实验室、复旦大学公共卫生学院流行病学教研室国家卫生健康委员会卫生技术评估重点实验室、复旦大学公共卫生学院流行病学教研室国家卫生健康委员会卫生技术评估重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
![表2 Tg基因rs180195位点基因型和等位基因频率在对照组和抗体阳性组间的比较[例数(%)]](http://bookimg.mtoou.info/tubiao/gif/XJYI202008001_02300.gif)