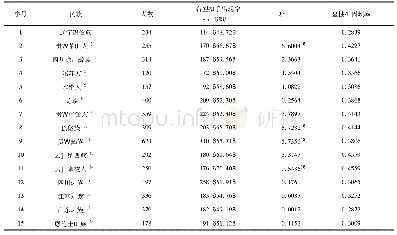
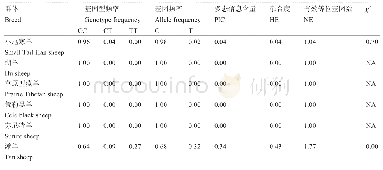
《表2 4 个候选SVs在藏-汉群体中等位基因频率Tab.2AlelefrequenciesofthefourcandidateSVsinTibetanandHanChinesepopulations
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《基因组结构变异与藏族高原适应表型的遗传相关性初探》
4个SVs在藏汉两个群体中的基因分型结果发现,位于chr1:220502944-220503583上的长度为639bp缺失、chr7:39387270-39387887上的长度为617 bp的缺失和chr19:31733651-31733771上的长度为120bp的缺失频率在藏族中都显著高于汉族中的频率。然而,位于chr9:7214431的长度为230 bp的插入的频率在藏汉群体中并没有显著的差异(见表2和图4)。
| 图表编号 | XD00168198600 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.03.01 |
| 作者 | 次旺拉姆、和耀喜、宿兵、欧珠罗布 |
| 绘制单位 | 西藏大学医学院、中国科学院昆明动物研究所遗传资源与进化国家重点实验室、中国科学院昆明动物研究所遗传资源与进化国家重点实验室、西藏大学医学院、西藏阜康医院 |
| 更多格式 | 高清、无水印(增值服务) |