《表2 EgWRKY蛋白理化性质分析》
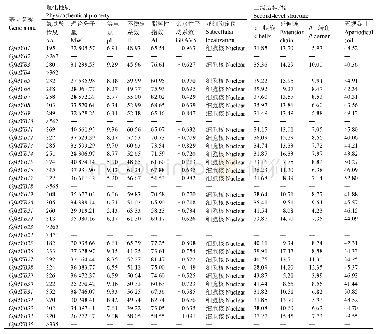
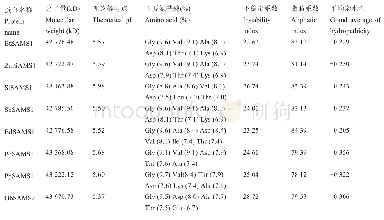
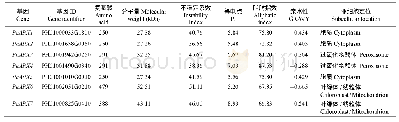
利用ProtParam在线软件(http://expasy.org/tools/protparam.html)分析EgWRKY蛋白的基本性质,预测结果如表2所示。95个WRKY蛋白中,56个蛋白的理论等电点(pI)小于7,39个蛋白的pI大于7,pI最小值为4.74(EgWRKY73),最大值为10.18(EgWRKY84),平均pI为7.15;EgWRKY25和EgWRKY56蛋白质的不稳定系数小于40,为稳定蛋白,其余93个EgWRKY蛋白的不稳定系数大于40,为不稳定蛋白,该结果表明EgWRKY转录因子家族大多为不稳定蛋白。利用NetPhos 3.1 Server在线软件(http://www.cbs.dtu.dk/services/NetPhos/)预测氨基酸序列磷酸化;利用DictyOGlyc 1.1 Server在线软件(http://www.cbs.dtu.dk/services/DictyOGlyc/)预测氨基酸序列的O-糖基化修饰情况,发现平均磷酸化位点有37.8个,O-糖基化位点有1.6个;利用ProtScale在线软件(https://web.expasy.org/protscale/)分析蛋白质的亲/疏水性,从EgWRKY蛋白的脂肪系数来看,该95个EgWRKY蛋白的脂肪系数均小于100,该结果表明其均为亲水性蛋白;利用SignalP5.0在线软件(http://www.cbs.dtu.dk/services/SignalP/)预测蛋白的信号肽,发现5个EgWRKY蛋白存在信号肽(EgWRKY29、EgWRKY38、EgWRKY45、EgWRKY63及EgWRKY87),为分泌蛋白;利用ProtComp 9.0(http://linux1.softberry.com/berry.phtml?topic=protcomppl&group=programs&subgroup=proloc)在线软件预测蛋白亚细胞定位,结果表明95个EgWRKY蛋白中有84个定位在细胞核中,占总蛋白的88.3%,11个在细胞质中,推测可能参与细胞质基因的转录调控;应用SOPMA在线软件(https://npsa-prabi.ibcp.fr/cgi-bin/np sa_automat.pl?page=npsa_sopma.html)预测蛋白的二级结构,发现所有EgWRKY蛋白的二级结构均有4种,即α-螺旋、β-转角、无规卷曲及延伸链,其中60个EgWRKY蛋白以α-螺旋为主要结构,无规卷曲为次要结构,35个以无规卷曲为主要结构,α-螺旋为次要结构,β-转角及延伸链所占比例较少。
| 图表编号 | XD00147722000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.07.01 |
| 作者 | 周丽霞、曹红星 |
| 绘制单位 | 中国热带农业科学院椰子研究所、海南省热带油料作物生物学重点实验室、中国热带农业科学院椰子研究所、海南省热带油料作物生物学重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式