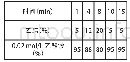
《表3 肝脏中五种算法评估结果》
注:同列数值越小表示基因越稳定,“*”表示本列中稳定内参基因。GeNorm为稳定性量度(M)值,BestKeeper为标准偏差(SD值),NormFinder为基因稳定值,ΔCt为平均标准偏差(Mean SD值),RefFinder为几何平均数加权(GM值)。Note:The lower the value the more stable the ge
肝脏中5种算法评估9个内参基因稳定性见表3,确定各种算法中4个最稳定内参基因。GeNorm评估4个最稳定内参基因为:B2m=Ywhaz>Ppia>Eef1a1,BestKeeper评估4个最稳定内参基因为:B2m>Ywhaz>Ppia>Eef1a1,NormFinder评估4个最稳定内参基因为:Gapdh>Sdha>Eef1a1>Ppia,ΔCt评估4个最稳定内参基因为:Gapdh>Eef1a1>Sdha>Ppia,RefFinder评估4个最稳定内参基因为:Gapdh>B2m>Ywhaz>Eef1a1。结果表明,每种算法评估最稳定内参基因不同,BestKeeper和GeNorm评估结果中3个基因(B2m,Ywhaz,和Eef1a1)与RefFinder相同,ΔCt和NormFinder结果中2个基因(Gapdh和Eef1a1)与RefFinder相同。5种算法中Hprt1、Actb和Rpl5均为不稳定内参基因,表明其在模型中表达不稳定,不适合标准化该模型qPCR数据。
| 图表编号 | XD0014058600 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2018.12.25 |
| 作者 | 张震、姜恩泽、宁方勇、杜智恒、白秀娟 |
| 绘制单位 | 东北农业大学动物科学技术学院、东北农业大学动物科学技术学院、东北农业大学动物科学技术学院、东北农业大学动物科学技术学院、东北农业大学动物科学技术学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式