《表2 SCMV分离物中基因组区域的核苷酸和氨基酸同源性》
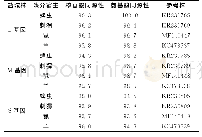
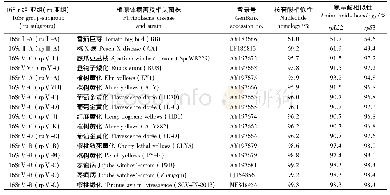
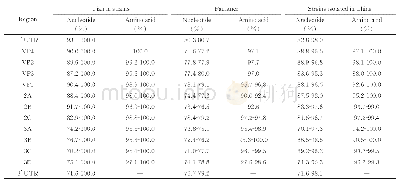
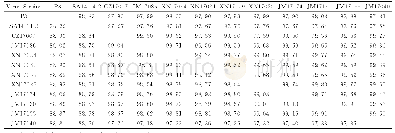
本研究采用“先分段扩增再拼接全长”传统基因组扩增方法,对测序结果进行了比对和拼接,拼接完成的SCMV基因组通过BLAST分析(https://www.ncbi.nlm.nih.gov/)发现,35个SCMV分离物同在线SCMV的氨基酸和核苷酸一致率均为100%,有1份分离物(命名为Shanxi_2)与所有报道SCMV分离物在氨基酸和核苷酸水平均有差异,是1个新的SCMV分离物。该分离物全基因组全长9 539 bp,3'-UTR端长233 bp,5'-UTR端长114 bp,包含一个大的开放阅读框,推定的ORF从ATG(115~117 bp)开始,编码一个含有3 063个氨基酸的多聚蛋白,分子量为346.193 k Da。通过与已公开的SCMV序列比对发现该多聚蛋白可以被切割为10个成熟的蛋白(图1),分别为(P1、Hc-Pro、P3、6K1、CI、6K2、NIa-Vpg、NIa-Pro、Nib、CP)。结合在线的8个SCMV基因组,对SCMV进行了一致率分析。结果显示这9个分离物的CP基因间核苷酸同源性最高为92.8%~95.3%(表2),CI基因间氨基酸同源性最高为97.6%~98.3%,P1基因间核苷酸和氨基酸同源性最低分别为85.7%~89%、90.6%~94.8%。该结果表明,在核苷酸水平CP保守性最高,在氨基酸水平CI保守性高,而P1蛋白在氨基酸与核苷酸水平保守性均低。
| 图表编号 | XD0092162200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.09.01 |
| 作者 | 张虎、景晓雅、孙柳清、崔爱民、张鹏华、单皓、陈伟 |
| 绘制单位 | 山西省农业科学院小麦研究所、山西师范大学生命科学学院、山西师范大学生命科学学院、山西省农业科学院小麦研究所、山西省农业科学院小麦研究所、山西省农业科学院小麦研究所、山西师范大学生命科学学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式