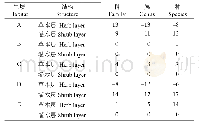
《表2 不同物种的ISWI、CHD复合体组成》
目前对染色质重塑复合体的作用机制并不十分清楚。一般认为,染色质重塑复合体ATPase亚基与DNA易位酶(DNA translocases)具有相似之功能。当染色质重塑复合体ATPase亚基与核小体结合后,其易位酶活性将核小体之间的连接DNA(linker)推向核小体核心结构,使DNA形成一个环状结构(loop),从而使DNA与组蛋白之间结合由“紧密”状态变为“松散”状态[24–27]。该过程可能同时产生很多环状结构,这些环状结构只需改变DNA与1~2个组蛋白的结合程度即可启动核小体的滑动。然而,对形成的环状结构大小并不十分清楚,目前的证据支持该环状结构可能由较多的碱基(约100 bp)组成[28]。而关于染色质重塑是如何被精确调节的还知之甚少,该过程可能与组蛋白的翻译后修饰有关。如H4尾巴第17~19位残基乙酰化能提高蟾蜍(Xenopus laevis)ISWI复合体催化活性[29–30],而H4K16ac则抑制其活性。对酵母yISW2(ISWI复合体催化亚基)和yChd1(CHD复合体催化亚基)而言,H4乙酰化抑制其ATPase活性而不响应它与核小体结合,然而H4乙酰化却能提高酵母RSC复合体(SWI/SFN类)的重塑活性[31]。
| 图表编号 | XD0093016600 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.09.01 |
| 作者 | 彭锈玲、王剑豪、杨松光 |
| 绘制单位 | 中国科学院华南植物园华南农业植物分子分析与遗传改良重点实验室、中国科学院大学、中国科学院华南植物园华南农业植物分子分析与遗传改良重点实验室、中国科学院大学、中国科学院华南植物园华南农业植物分子分析与遗传改良重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式