《表1 正交试验设计:葛根SRAP-PCR反应体系的优化及引物筛选》
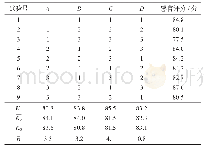
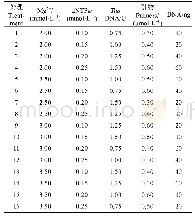
根据正交设计的扩增结果对各个组合进行打分,发现处理10扩增条带多而清晰,处理9和13仅有引物二聚体而无扩增条带(图1)。通过对16个体系的3次重复扩增产物进行打分,计算平均值,获得各因素各处理的Ki值及极差R值(表1)。结果显示,DNA和Mg2+浓度的K2值最大,dNTP和引物浓度的K3值最大,Taq DNA聚合酶的K1值最大。Ki越大,表明该水平效果最好(桂腾琴等,2009;严华兵等,2016)。因此,确定葛根最佳SRAP-PCR反应体系为:DNA 40 ng,Mg2+1.5 mmol/L,dNTPs 0.25 mmol/L,引物0.6μmol/L,Taq DNA聚合酶0.5 U。DNA、Mg2+、dNTP、引物、Taq DNA聚合酶的R值分别为3.0、4.5、5.1、4.1、4.9。R值越大,表明该因素的影响越大(桂腾琴等,2009;严华兵等,2016)。因此,葛根SRAP-PCR反应的各因素影响顺序为:dNTP>Taq DNA聚合酶>Mg2+>引物>DNA浓度。
| 图表编号 | XD0087021200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.08.28 |
| 作者 | 尚小红、严华兵、曹升、谢向誉、张尚文、王艳、欧昆鹏 |
| 绘制单位 | 广西壮族自治区农业科学院经济作物研究所、广西壮族自治区农业科学院广西作物遗传改良生物技术重点开放实验室、广西壮族自治区农业科学院经济作物研究所、广西壮族自治区农业科学院经济作物研究所、广西壮族自治区农业科学院广西作物遗传改良生物技术重点开放实验室、广西壮族自治区农业科学院经济作物研究所、广西壮族自治区农业科学院广西作物遗传改良生物技术重点开放实验室、广西壮族自治区农业科学院生物技术研究所、广西壮族自治区农业科学院生物技术研究所、广西壮族自治区农业科学院生物技术研究所 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式