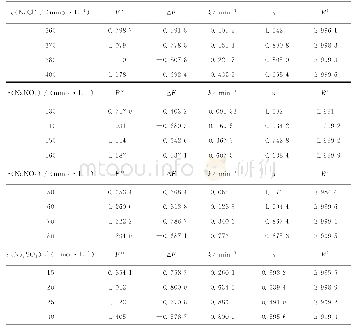
《表1 不同盐影响下还原变性溶菌酶聚集动力学曲线拟合参数Tab.1 Fitting results for the kinetic traces of reduced-denatured lysozy
对于蛋白聚集速率和盐浓度的相关性,笔者对表1中的数据进行了分析.在图3中将不同盐浓度下获得的蛋白聚集速率和盐浓度作图.发现除Na2SO4体系30mmol/L数据点外,对于4种盐而言,随着盐浓度的增加,蛋白聚集速率k呈现递增趋势.对这些数据进行线性相关分析,即用每组盐的动力学拟合结果的k值对盐浓度进行作图,并用y=a+bx方程分别对k与浓度关系进行线性回归分析.回归拟合结果显示出良好的线性关系.此外,对表征蛋白聚集复杂性的n对盐浓度作图,发现也存在类似的相关规律,相关结果也示于图3,线性拟合获得的斜率和截距等拟合参数列于表2.对于Na2SO4体系30mmol/L这个偏低的数据点,笔者认为可能由于该条件下动力学实验存在的固有误差所致.从图2d可以看出,30mmol/L条件下Na2SO4体系聚集过快,在动力学实验的死时间30s内就已经发生很大程度的聚集,这使得所测的该条件下的动力学曲线由于数据点的缺失而有所失真,这应该是Na2SO4体系30 mmol/L这个数据点偏低的原因.
| 图表编号 | XD0023817500 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2018.11.25 |
| 作者 | 贾宝环、于洋、王悦、刘思阳、杜保安、马刚 |
| 绘制单位 | 河北大学化学与环境科学学院药物化学与分子诊断教育部重点实验室、河北大学化学与环境科学学院药物化学与分子诊断教育部重点实验室、河北大学化学与环境科学学院药物化学与分子诊断教育部重点实验室、河北大学化学与环境科学学院药物化学与分子诊断教育部重点实验室、河北大学化学与环境科学学院药物化学与分子诊断教育部重点实验室、河北大学化学与环境科学学院药物化学与分子诊断教育部重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
查看“表1 不同盐影响下还原变性溶菌酶聚集动力学曲线拟合参数Tab.1 Fitting results for the kinetic traces of reduced-denatured lysozyme aggregation by dif”的人还看了
-

- 表3 BPA在柏树枝生物炭上吸附的2种动力学模型拟合参数Tab.3 Fitting parameters of two kinds kinetic models for BPA adsorption on cypress biochars
-
![表2 TETA-[Cu3 (BTC) 2]吸附Pb (II) 和Cd (II) 动力学拟合参数Tab.2 Fitting parameters for adsorption kinetics of Pb (II) and Cd (II) o](//bookimg.mtoou.info/tubiao/gif/SCLJ201901013_14500.gif)
- 表2 TETA-[Cu3 (BTC) 2]吸附Pb (II) 和Cd (II) 动力学拟合参数Tab.2 Fitting parameters for adsorption kinetics of Pb (II) and Cd (II) o
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式


![表2 TETA-[Cu3 (BTC) 2]吸附Pb (II) 和Cd (II) 动力学拟合参数Tab.2 Fitting parameters for adsorption kinetics of Pb (II) and Cd (II) o](http://bookimg.mtoou.info/tubiao/gif/SCLJ201901013_14500.gif)


