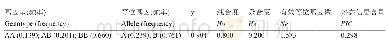《表3 CraYVV基因组结构中基因间隔区和各基因的遗传结构及中立性分析结果》
s:分离位点数目;Eta:突变总数;k:核酸差异平均数;π:核苷酸多态性;θ-w:基于分离位点数目估算的种群突变率;θ-Eta:基于突变总数估算的种群突变率。s:Total number of segregating sites;Eta:total number of mutations;k:average number of nucleotide differences
CraYVV核苷酸多态性指数π分析结果显示,CraYVV中C1基因的π值最高,其次是基因间隔区和C4;基于分离位点数目估算的种群突变率θ-w以及基于突变总数估算的种群突变率θ-Eta分析结果也显示,CraYVV中C4基因的θ-w数值最高,其次是C1基因和基因间隔区;CraYVV中C1基因的θ-Eta数值最高,其次是C4基因和基因间隔区;V1、V2、C2、C3的π、θ-w和θ-Eta数值都较低(表3)。表明CraYVV中C1基因核苷酸突变引起的变异较其它基因和非编码区大,其次是C4基因及基因间隔区;V1、V2、C2、C3基因序列则较为保守,这与CraYVV不同分离物间的相似性比较结果相吻合。
| 图表编号 | XD00181426200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.06.01 |
| 作者 | 赵丽玲、施章吉、李婷婷、钟静、丁铭、张仲凯 |
| 绘制单位 | 云南省农业科学院生物技术与种质资源研究所云南省农业生物技术重点实验室、云南省农业科学院生物技术与种质资源研究所云南省农业生物技术重点实验室、云南省农业科学院生物技术与种质资源研究所云南省农业生物技术重点实验室、云南省农业科学院生物技术与种质资源研究所云南省农业生物技术重点实验室、云南省农业科学院生物技术与种质资源研究所云南省农业生物技术重点实验室、云南省农业科学院生物技术与种质资源研究所云南省农业生物技术重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式