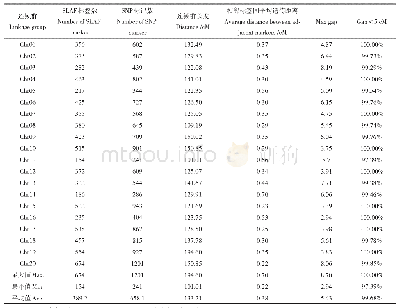
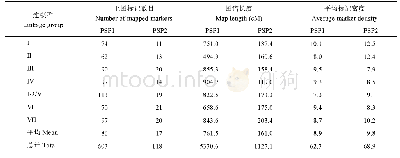
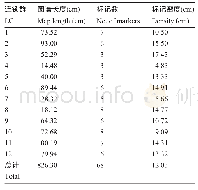
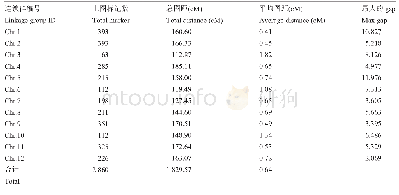
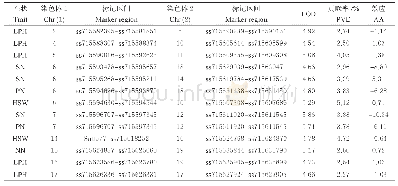
《表5‘Y两优2号’RIL群体遗传图谱基本信息》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《超级杂交稻‘Y两优2号’耐冷性QTL定位与杂种优势分析》
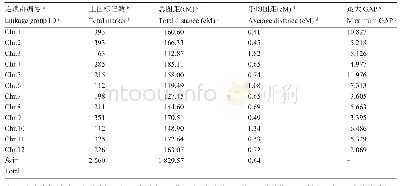
注:a:连锁群编号与基因组的编号一致;b:上图总标记数表示一条连锁群上的标记的总数目;c:总图距,表示一条连锁群上标记的总遗传距离;d:平均图距表示平均一条连锁群上标记的平均遗传距离;e:最大GAP表示连锁群中Block之间的最大距离,最大gap越小,表示图谱越均匀
本研究中使用的种质通过全基因组测序进行基因分型。总共有2.3 M双等位基因SNP,选择次等位基因频率(minor allele frequency,MAF)≥5%用于关联作图。在本研究中,首先使用R V3.2.1的分位数-分位数图标准函数对tcl的值进行归一化。然后,使用在GEMMA中实施的线性混合模型进行GWAS分析。为了进一步纠正种群结构并减少假阳性,对种群进行了PCA分析,并按照Wang等(2016b)的方法,在GWAS分析中使用前4个主成分作为协变量。之后使用置换策略来确定基因组水平的显著SNP。在200次重复之后,选择10-5的p值作为阈值,以确保错误发现率小于5%。使用Haploview V4.2进行连锁不平衡(linkage disequilibrium,LD)分析,并且按照Gabriel等(2002)的方法在r2值的95%置信区间超过0.98并且下限超过0.70时产生LD块。最后选择LD区块中鉴定的基因作为控制tcl的潜在候选基因。
| 图表编号 | XD00152842300 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.04.14 |
| 作者 | 刘友发、常硕其、常天根、欧阳翔、邓启云、夏石头、朱新广 |
| 绘制单位 | 湖南农业大学植物激素与生长发育湖南省重点实验室、湖南杂交水稻研究中心、湖南杂交水稻研究中心、中国科学院分子植物科学卓越创新中心植物生理生态研究所、湖南杂交水稻研究中心、湖南袁创超级稻技术有限公司、湖南农业大学植物激素与生长发育湖南省重点实验室、中国科学院分子植物科学卓越创新中心植物生理生态研究所 |
| 更多格式 | 高清、无水印(增值服务) |