《表1 反硝化与厌氧氨氧化功能基因引物》
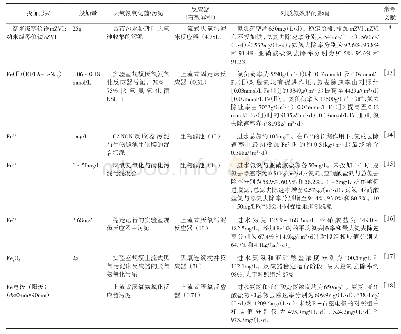
采用FastDNA Spin Kit(MP,Biomedicals,CA,USA)从0.5 g经冷冻干燥的土壤/沉淀物样品中进行细菌DNA的提取.使用Nanodrop 2000UV-Vis分光光度计(Thermo Scientific,USA)检测提取DNA的浓度和纯度.为比较各土壤样品中功能基因的绝对丰度,在ABI 7500系统(Applied Biosystems,Foster City,CA,USA)中进行反硝化功能基因nir S、nirK和nosZ,厌氧氨氧化功能基因ANAMMOX bacterial 16S rRNA(amx)[16~18]的qPCR分析,细菌16S rRNA高变区V4/V5段扩增的正向引物是515F(5'-GTGCCAGCMGCCGCGG-3'),反向引物是907R(5'-CCGTCAATTCMTTTRAGTTT-3')[19],各功能基因引物信息如表1所示;反应体系为:2X Taq Plus Master Mix 10μL,引物F(5μmol·L-1)0.8μL,引物R(5μmol·L-1)0.8μL,模板DNA 1μL,ddH2O7.4μL;反应条件为:95℃预变性5 min,循环1次,95℃变性30 s,退火30 s(nir S、nir K、nosZ和amx退火温度分别为50、55、58和50℃),循环35次,72℃延伸1 min.使用纯化后的PCR样品在上海美吉生物医药科技有限公司的Illumina Mi Seq测序平台(Illumina Inc.,USA)进行测序,所得到的数据在该公司I-Sanger云平台(www.i-sanger.com)分析,去除低质量序列并进行筛分后,选用相似水平为97%的OTU样本,最终可得到微生物群落组成信息,即不同细菌的相对占比.
| 图表编号 | XD00118279700 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.01.15 |
| 作者 | 陈志浩、覃云斌、丁帮璟、胡优优、陈湜、李正魁 |
| 绘制单位 | 南京大学环境学院污染控制与资源化研究国家重点实验室、南京大学环境学院污染控制与资源化研究国家重点实验室、南京大学环境学院污染控制与资源化研究国家重点实验室、南京大学环境学院污染控制与资源化研究国家重点实验室、南京大学环境学院污染控制与资源化研究国家重点实验室、南京大学环境学院污染控制与资源化研究国家重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式