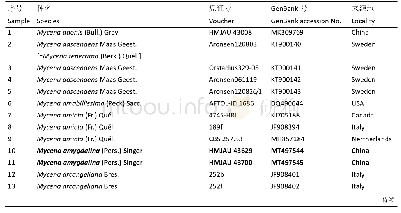
《表1 分子系统发育分析采用的乳菇属分类信息和GenBank数据》
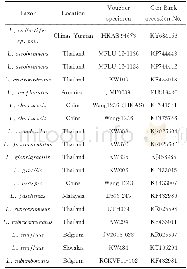
PCR扩增产物送北京测序公司进行正反方向测序(IOMARRY),所得正反序列在SeqMan Pro(DNASTAR,Madison,WI)中合并和修剪。然后在MAFFTversion 7中进行多重比对[15],并在BioEdit v.7.0.4中对序列进行手动修剪[16],然后在Gblocks 0.91b中对齐并剪切掉部分质量差的位点[17],ITS1、5.8S和ITS2用于系统发育树分析,所有序列信息见表1。选择L.hirtipes J.Z.Ying,(Fr.) Fr.,L.gracilis Hongo和L.glabrigracilis Wisitr.&Nuytinck三个种为外类群。最大相似性分析(Maximum likelihood (ML)) 在网站CIPRES中RAxML-HPC2XSEDE(8.2.10)系统中进行[18-20],采用GTRGAMMA模型,1000次重复。贝叶斯分析(Bayesian analysis)在MrBayes 3.2中运行[21,22],在MrModeltest 2.3中通过hLRT的得到GTR+I+G模型[23]。贝叶斯分析(BI)运行50,000,000代,最终得到最优系统发育树形,结果见图1。
| 图表编号 | XD0013708500 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2018.04.01 |
| 作者 | 罗侠 |
| 绘制单位 | 滁州学院生物与食品工程学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式