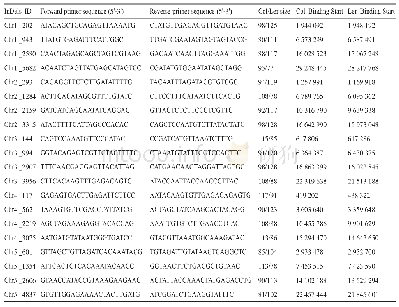
《表2 PHRE7及其拷贝在毛竹基因组的命名及位置》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《毛竹Phyllostachys edulis retrotransposon 7(PHRE7)转座子的克隆与鉴定》
PHRE7转座子全长为6 073 bp,测序结果与预测一致。PHRE7转座子组成为5′端和3′端的长末端重复序列和含5种酶的连续开放阅读框(ORF),结构顺序依次为5′-L-LTR-GAG-PR-INT-RT-RH-LTR-R-3′(图2)。各结构长度具体如下:左端LTR(L-LTR)长度为959 bp,右端LTR(LTR-R)为3′端LTR的反向重复序列,长度也为959 bp,相似性为96.7%。计算得插入时间约为126.92万a前。开放阅读框核苷酸编码区总长度为1 524 bp,共编码氨基酸507个,GAG核心区位置在1 030~1 744 bp,主要与反转录转座子RNA的成熟和包装有关;PR核心区为是水解酶的编码区,位置在1 978~2 224 bp,与反转录后多聚蛋白前体切割为功能性多肽有关;INT核心区是整合酶的编码区,位置在2 365~3 004 bp,用于催化反转录转座子插入宿主基因组的整个过程[33];RT核心区是反转录酶的编码区,位置在3 580~4 312 bp,用于催化单链RNA或DNA合成DNA的过程,是转座子转座的必不可少的酶;RH核心区位置在4 624~5 020 bp,用于编码核糖核酸酶H。核糖核酸酶H是水解酶的一种,负责原始RNA模板的水解。根据编码区结构顺序GAG-PR-INT-RT-RH,可确定PHRE7反转录转座子是Ty1-gypsy家族成员。通过cd-hit软件[26]对比毛竹基因组中的转座子,鉴定出PHRE7相似的序列,即其拷贝。结果显示:PHRE7存在相似的其他10个拷贝,根据拷贝位置不同,分别把10个拷贝命名(表2)为PHRE7-1,PHRE7-2,PHRE7-3,PHRE7-4,PHRE7-5,PHRE7-6,PHRE7-7,PHRE7-8,PHRE7-9和PHRE7-10,10个拷贝的结构也相对完整(图2)。
| 图表编号 | XD0098805200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.10.20 |
| 作者 | 蒋政勤、周明兵、郑浩、季航、徐芷馨 |
| 绘制单位 | 浙江农林大学省部共建亚热带森林培育国家重点实验室、浙江农林大学省部共建亚热带森林培育国家重点实验室、浙江农林大学浙江省竹资源与高效利用协同中心、浙江农林大学省部共建亚热带森林培育国家重点实验室、浙江农林大学省部共建亚热带森林培育国家重点实验室、浙江农林大学省部共建亚热带森林培育国家重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |