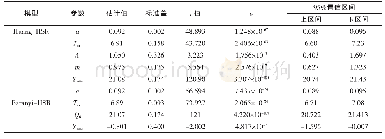
《表1 Baranyi-HSR模型的统计分析》
通过一步法分别对低浓度接种的优势菌群的生长数据(共计166数据点)和高浓度接种的优势菌群生长数据(共计157数据点)进行拟合分析,同步构建初级模型(Baranyi模型)和二级模型(HSR模型),估计菌株最大生长浓度Ymax、迟滞期相关表征参数Q0,及二级模型系数a,即=(6,(4,。统计分析和参数估计结果如表1和表2所示。由表1可知,低浓度和高浓度菌群接种状态下,所构建的Baranyi-HSR模型的均方根误差(root mean square error,RMSE)分别为0.55、0.48 log CFU/g,F检验表明模型可用于描述金枪鱼样品中优势菌群的生长(P<0.05)。由表2可知,低浓度接种和高浓度接种状态下,一步法估计的菌群最大生长浓度分别为21.95 ln CFU/g(或9.53 log CFU/g)和22.65 ln CFU/g(或9.83 log CFU/g),两者仅相差0.70 ln CFU/g(或0.30 log CFU/g),无显著差异;低浓度接种时,Q0值为?2.036,其P值2.95×10?6;高浓度接种时,Q0值为?0.647,虽然该估计值可靠性不高(P=0.217),但仍能用于菌群迟滞期状态的描述;低浓度接种和高浓度接种状态下,二级模型系数a值分别为0.077和0.071,两者仅差7.8%,亦无显著差异。
| 图表编号 | XD00207295100 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.12.25 |
| 作者 | 张子叶、李晓婷、刘丽敏、庄滢钰、闫晓彤、黄晓燕、方婷、李长城 |
| 绘制单位 | 福建农林大学食品科学学院、福建农林大学食品科学学院、福建农林大学食品科学学院、福建农林大学食品科学学院、福建农林大学食品科学学院、福建农林大学食品科学学院、福建农林大学食品科学学院、福建农林大学食品科学学院 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式