《表1 3个样品全基因组重亚硫酸盐测序数据统计汇总》
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式
本系列图表出处文件名:随高清版一同展现
《缺氮胁迫对固氮蓝藻鱼腥藻PCC7120 DNA甲基化修饰模式的影响》
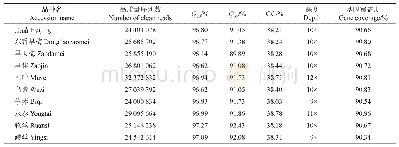
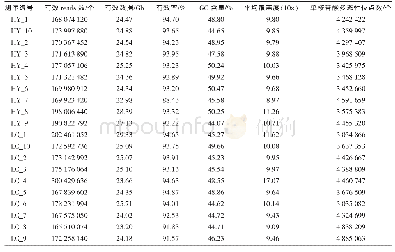
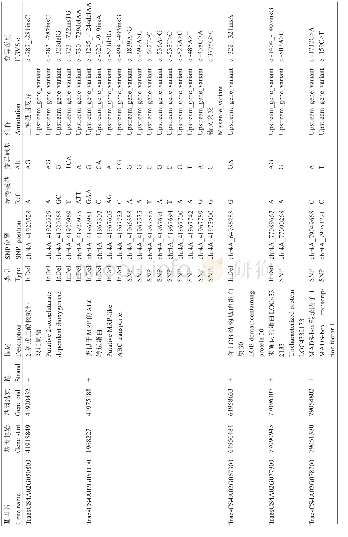
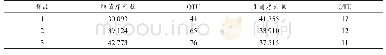
完成全基因组重亚硫酸盐测序后,正常氮藻丝、缺氮藻丝和异形胞基因组分别获得了6.48,8.85,7.56Gb的原始数据(raw data)(表1)。经过数据整理(trimming)后,分别得到6.25,8.38,7.11Gb的干净数据;3个样品的重亚硫酸盐转化率达到99.84%~99.85%;比对到参考基因组上的读长占总干净读长的比例达到94.68%~95.82%,其中重复序列比率仅为10.61%~13.62%;平均覆盖深度达到743.73~952.1(表2);基因组上大于等于10×测序深度的碱基数占基因组总长的比例达到99.13%~99.14%;基因组胞嘧啶位点的平均覆盖深度达到262.2~328.4。这些结果表明,测序时重亚硫酸盐转化完全,测序质量和覆盖度达到要求,测序结果可以用于后续分析。
| 图表编号 | XD0076359200 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2019.08.01 |
| 作者 | 胡浪、郭青青、刘烨蓉、胡章立、王江新、雷安平 |
| 绘制单位 | 深圳大学生命与海洋科学学院、深圳市海洋生物资源与生态环境重点实验室、深圳市海洋藻类生物开发与应用工程实验室、广东省植物表观遗传学重点实验室、深圳大学生命与海洋科学学院、深圳市海洋生物资源与生态环境重点实验室、深圳市海洋藻类生物开发与应用工程实验室、广东省植物表观遗传学重点实验室、深圳大学生命与海洋科学学院、深圳市海洋生物资源与生态环境重点实验室、深圳市海洋藻类生物开发与应用工程实验室、广东省植物表观遗传学重点实验室、深圳大学生命与海洋科学学院、深圳市海洋生物资源与生态环境重点实验室、深圳市海洋藻类生物开发 |
| 更多格式 | 高清、无水印(增值服务) |