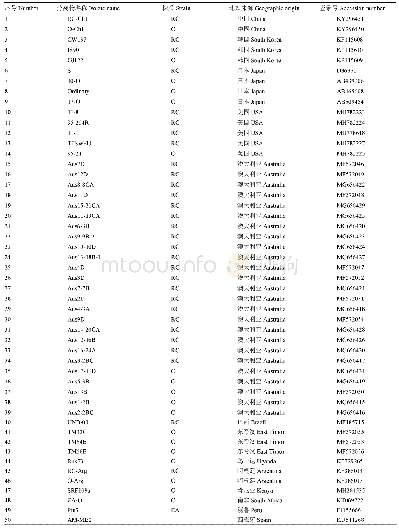
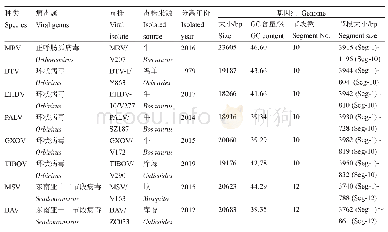
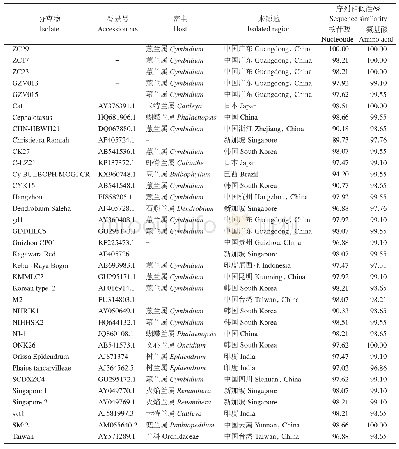
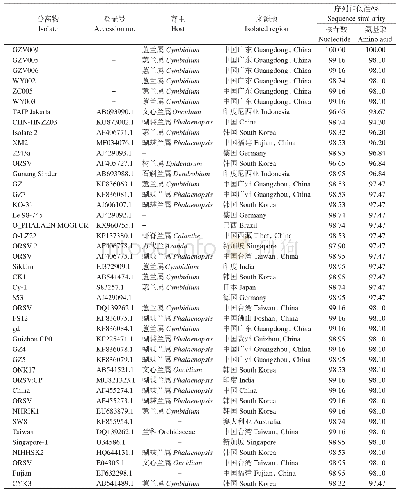
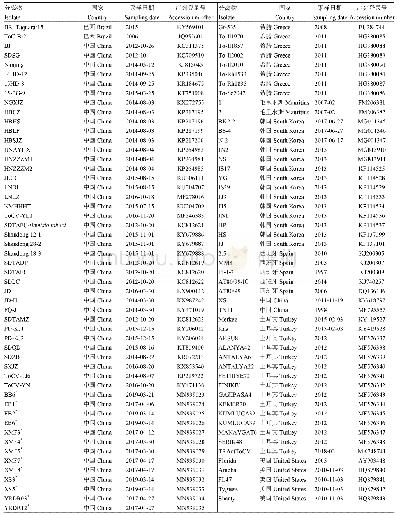
《表1 本研究用到的ToCV分离物信息》
*:本研究测序的分离物Isolates sequenced in this study
测序获得的序列采用DNAMAN(Lynnon BioSoft,Canada)、BLAST等软件进行序列分析。除了新测序获得的13条CP基因序列外,从GenBank下载带有采样时间和地理信息的90个分离物相应的核苷酸序列合并得到103条CP基因序列(表1)。使用PhyloSuite 1.16[26]中的MAFFT算法[27]基于密码子进行多重序列比对。由于重组可能导致过快或假阳性的进化速率[28],为排除重组对进化速率的影响,采用两种不同的方法检测ToCV CP中的重组事件。首先应用SplitsTree4.13.1[29]基于邻接网络算法重建系统发育网络以检测数据集是否存在重组,随后通过RDP 4.97软件包的7种算法(RDP、GENECONV、BOOTSCAN、MAXCHI、CHIMAERA、SISCAN和3SEQ)[30]进行重组分析。
| 图表编号 | XD00202382000 严禁用于非法目的 |
|---|---|
| 绘制时间 | 2020.12.01 |
| 作者 | 邹林峰、涂丽琴、沈建国、杜振国、蔡伟、季英华、高芳銮 |
| 绘制单位 | 福建农林大学植物病毒研究所福建省植物病毒学重点实验室、江苏省农业科学院植物保护研究所、福州海关技术中心、福建农林大学植物病毒研究所福建省植物病毒学重点实验室、榕城海关综合技术服务中心、江苏省农业科学院植物保护研究所、福建农林大学植物病毒研究所福建省植物病毒学重点实验室 |
| 更多格式 | 高清、无水印(增值服务) |
 提示:宽带有限、当前游客访问压缩模式
提示:宽带有限、当前游客访问压缩模式